진화
| 생물학 관련 문서 |
| 진화 |
|---|
 |
| 진화 과정 |
| 연구 및 역사 |
| 진화 이론의 주요 분야 |
| 주요 학자 |
진화(進化, 영어: evolution)는 생물 집단이 여러 세대를 거치면서 변화를 축적해 집단 전체의 특성을 변화시키고 나아가 새로운 종의 탄생을 형성하는 관찰된 자연 현상을 가리키는 생물학 용어이다.[1] 여러 생물 종 사이에서 발견되는 유사성을 통해 현재의 모든 종이 이러한 진화의 과정을 거쳐 먼 과거의 공통 조상, 즉 공통의 유전자 풀로부터 점진적으로 분화되어 왔다는 사실을 유추할 수 있었고,[2] 이러한 종분화가 직접적으로 관찰됨에 따라[3], 진화는 현재 관찰된 자연 현상으로서 과학계에 알려져 있다.
진화는 세대에서 세대로 유전형질이 전달되는 도중에 일어나는 유전자의 변화가 누적된 결과이다. 유전자 변화가 일어나는 요인은 돌연변이와 유성생식에 의한 유전자 재조합 등이다. 이를 통해 종분화가 일어나며, 그 과정에서 다른 종들이 분리가 된다. 예를 들어 쥐와 다람쥐의 공통 조상으로부터 현재의 쥐가 갈라져 나왔고, 원숭이와 인간의 공통조상으로부터 점진적으로 종분화가 일어나 현재의 인간종이 탄생했다라고 할 수 있다.
진화가 일어나는 주요 작동 기제는, 생물 집단과 환경의 상호 관계에 의해 유전형질이 선택되는 자연선택과, 집단 안에서 이루어지는 유전자 부동이다. 자연선택으로 인해 생물 집단이 환경에 적응하는데 유리한 유전형질은 다음 세대로 전달되고 불리한 형질은 사라지게 된다.[4] 한편, 유전자 부동은 독립적인 유전형질들이 생존하고 재생산할 수 있는 기회를 지속적으로 제공한다.[5] 이러한 진화의 과정을 거쳐 생물들은 환경에 적응하여 새로운 종들로 분화한다. 생물들 사이의 상호 작용에 의한 진화의 결과로는 공진화와 공생이 있다. 급격한 환경의 변화 등은 생물의 멸종으로 이어지기도 한다.
진화생물학은 생물 집단에서 일어나고 있는 진화 현상을 연구하여 진화의 원인을 규명하는 과학 이론을 정립하는 학문이다. 진화생물학은 19세기 무렵 화석과 생물 다양성에 대한 연구를 통해 종의 변화에 대한 여러 이론들이 제시됨으로써 출발하였다.[6] 오늘날의 진화생물학은 찰스 다윈과 알프레드 러셀 월리스가 1858년 공동으로 집필한 논문에서 자연선택의 개념에 기초하고 있다. 이 이론은 다윈이 1859년 출판한 책 《종의 기원》을 통해 널리 알려지게 되었다.[7] 시간이 지남에 따라 다윈의 진화이론은 과학자들 사이에서 폭넓게 받아들여지게 되었다.[8][9] 1930년대 무렵 과학자들은 다윈의 자연선택 이론과 멘델의 유전학을 조합하여 진화론을 한층 발전시켜 현대 진화 이론을 제시하였다. 현대 진화론에서 "진화"는 생물 집단 내에서의 유전자의 빈도가 세대가 지남에 따라 변화하는 것으로 정의된다.[10]
20세기 후반 이후 진화생물학의 연구 분야는 여러 방향으로 확산되었다. 로널드 피셔 등에 의해 시작된 집단유전학은 진화의 작동 기제에 대한 보다 세밀한 이론을 제시하고 있다. 집단유전학이 제시한 유전자 부동은 오늘날 진화를 이해하는 필수적인 개념이 되었으며, 하디 와인버그 평형은 생물 종의 유지와 분화의 요인을 탁월하게 설명하는 이론을 제시한다. 한편 수평적 유전자 이동의 발견은 생물 진화의 계통도를 완전히 바꾸어 놓았다. 오늘날의 진화 계통도는 다윈이 제시했던 생명의 나무를 폐기하고 다양한 생물의 유전자들이 얽힌 그물 모습으로 변했다. 기무라 모토는 유전적 부동을 진화의 중요한 요인으로 파악하는 중립 진화 이론을 제시하였다.[11]
스티븐 제이 굴드는 진화의 역사와 고생물에 대한 연구를 근거로 단속평형설을 제기하였다. 단속평형설은 종분화가 환경의 급격한 변화와 같은 특정한 이유가 발생할 때 급격히 이루어지며 그렇지 않을 때에는 오랜 기간 동안 종들이 유지된다는 이론이다. 리처드 도킨스는 진화의 결과 생물 집단이 얼마나 생존과 재생산에 성공하는가를 척도로 하는 진화도의 개념과 진화 과정에서 이루어지는 자연선택을 집단 단위로 파악하는 선택 단위의 개념을 제시하였다. 도킨스는 유전자와 진화의 관계를 놓고 스티븐 로즈와 논쟁을 벌이기도 하였다.[11]
오늘날 진화에 관련된 학문들은 여러 가지 갈래로 나뉘어 심층적으로 연구되고 있다. 더 많은 증거들이 발견되고 진화 과정에 대한 이해가 깊어짐에 따라 진화는 생물학을 체계화하는 핵심적인 원리가 되었다.[12][13] 또한 고속진화를 비롯한 종분화가 관찰됨으로써[14][15], 단순한 증명된 생물학 이론을 넘어 "관찰되는 사실" 및 자연 현상으로 인정되고 있으며, 현재 과학계에서는 진화라는 자연현상이 일어나는 속도를 결정하는 요인에 대한 연구가 많이 이루어지고 있다.[16]
진화유전학[편집]

생물의 진화는 유전되는 생물학적 특성에 변화가 일어나 발생한다. 인간을 예로 들면 눈의 색과 같이 유전되는 특성을 말한다. 사람 눈동자의 색은 부모 중 한 명으로부터 물려받는다.[17] 유전적 특성은 유전자에 의해 조정된다. 특정 개체의 게놈에 담겨있는 온전한 유전자 조합 전체를 유전형질이라 한다.[18]
한편 특정 개체를 통해 발현되어 관찰할 수 있는 유전적 특성은 발현형질이라 한다. 발현형질은 유전형질과 환경의 상호 관계에 의해 형성된 것이라 할 수 있다.[19] 따라서 특정 개체의 발현형질 전체가 유전되는 것은 아니다. 일광욕에 의해 피부가 어둡게 변했다고 어두운 피부가 유전되지는 않는다. 즉, 발현형질은 유전형질에 영향을 주지 않는다. 그러나 피부의 색과 관련한 유전형질이 변화하면 이는 계속하여 유전된다. 단적인 예로 돌연변이의 일종인 피부백변증을 들 수 있다. 피부 백변증이 있는 사람은 화상을 입을 정도로 햇볕에 노출되더라도 피부색이 어두워지지 않는다.[20]
유전되는 특성은 DNA에서 분자 규모의 유전 정보로 기록되어 세대에서 세대로 전해진다. 네 종류의 뉴클레오타이드를 기반으로 하는 중합체인 DNA는 유전 정보를 담는 유전자를 이룬다. 세포 내에서 유전자들은 염색체 단위로 존재한다. 개체 간의 서로 다른 DNA 염기 서열은 서로 다른 유전자를 만들게 되고, 서로 다른 유전자는 결국 서로 다른 유전적 특성을 만들게 된다. DNA 서열에서 같은 위치에 놓이는 서로 다른 뉴클레오타이드 서열은 결국 각각의 개체들이 다양한 유전적 특성을 지니게 한다. 이와 같은 유전적 특성을 대립형질이라 한다.[21][22] 멘델의 유전법칙은 완두콩의 대립형질을 관찰하여 발견한 것이다. 대립형질은 진화의 주요한 요소의 하나이다.
유전적 변이와 진화의 연관을 연구하는 학문을 진화유전학이라고 한다.[23]
오늘날에는 다양한 유전적 특성에 대한 연구가 광범위하게 진행되고 있다. ENCODE project라는 대규모의 비암호화 서열 연구로 인해, 암호화되지 않는 서열들의 진화 경로도 밝혀진 바 있으며, 그 각각의 기능자체가 진화되어오는 과정이 연구되었다.[24][25]
진화유전학의 최신 관심사는 진화의 속도로서 Accelerated Region이라 불리는 진화의 속도가 빨라진 특정 유전자 혹은 비암호화 서열의 트랜스포존이 될 수 있는 요소들을 연구하는 것이 포함된다. 이 부분들의 존재는 강력한 진화의 증거가 됨과 동시에, 진화의 속도를 연구하는 단서가 되며, 이런 부분들의 기능을 연구하는 수많은 과학자들은, 이것이 인간의 뇌 발달과 관련이 있다는 것을 밝혀내기도 했다.[26][27][28]
이뿐 아니라 유전자의 변화 없이 일어나는 유전형질의 변이를 다루는 후생유전학 분야 역시 진화와 관련하여 주목 받고 있다. 후생유전학에는 아직까지 밝혀지지 않은 많은 과제들이 많기 때문이다. H3K4me1(히스톤의 메틸화)의 패턴 분석을 통해, 진화의 방향을 결정하는 연구도 활발하게 진행되고 있다[29]
현대 진화학 연구는 주로 집단유전학(Population Genetics)으로 불리며, 다양성을 형성하는 유전적 부동, 변이, 선택에 관한 연구를 중심으로 진행된다. 2016년 미국유전학회(American Society of Human Genetics)에서는 새로이 개발된 기술들이 대거 발표됨으로써, 진화유전학이 새로운 전성기를 맞고 있음을 보여주고 있다.[30] 현대에도 진화의 과정은 직접 관찰이 가능해지면서, 이와같은 진화의 과정의 유전적 원인을 찾아내는 연구들이 활발해짐에 따라, 집단 유전학 역시 각광받고 있다.
개체차[편집]
진화는 개체차가 줄어드는 방향과, 늘어나는 방향이 뒤섞인 형태로 진행된다.
생물 개체의 발현형질은 유전형질과 환경의 상호 관계에 의한 결과이다. 개체간의 발현형질의 차이는 상당 부분 유전형질의 차이 때문이다.[22] 현대의 진화 이론은 유전형질의 차이에 의한 개체차를 진화의 기본적인 원인으로 본다. 임의적인 한 쌍의 대립형질을 생각해 볼 경우, 이 대립형질 쌍은 보다 일반적인 유전형질들과 관계를 맺으면서 진화의 압력을 받는다. 자연선택이 주는 효과가 대립형질 각각에게 미치는 영향이 동일하다면 대립형질의 발현빈도는 순전히 멘델의 유전법칙을 따를 것이다.
그러나 대립형질의 어느 한 쪽이 보다 환경적응에 유리하다면 세대를 거쳐감에 따라 점차적으로 유리한 유전형질을 갖는 개체가 많아질 것이고, 어느 한 세대가 되면 환경적응에 유리한 형질만이 살아 남아 고착될 것이다.[31] 이것이 바로 개체차가 줄어드는 방향이다.
반대로, 유전형질의 개체차는 다음과 같은 기작으로 다양화된다. 우선 유전자의 돌연변이에 의해서이다. 이러한 돌연변이는 또 다른 다양화 기작인 유성생식의 과정에서 일어나는 유전자 혼합, 또는 집단들 사이에서 일어나는 유전자 이동시에 함께 발생할 수 있다. 다른 종 사이에서 이루어지는 유전자 교환 역시 돌연변이를 일으킬 수 있다. 이종간 유전자 교환의 예로는 박테리아의 수평적 유전자 이동이나 식물의 잡종 등이 있다.[32] 이러한 유전형질의 변화가 종 자체의 정체성을 유지시켜주는 게놈에 주는 영향은 극히 적다.[33] 그러나 이러한 극히 작은 변화가 계속해서 일어날 경우 유전형질은 극적인 변화를 겪는다. 침팬지와 인간의 게놈은 단지 5%만이 다를 뿐이다.[34]
돌연변이[편집]

게놈에서 발생하는 무작위적인 돌연변이는 유전형질의 개체차를 일으킨다. 세포안의 게놈을 이루는 DNA 염기 서열은 감수 분열이나 DNA 복제의 과정에서 방사능, 바이러스, 트렌스포존, 그리고 돌연변이원이 되는 물질에 의해 돌연변이를 일으킬 수 있다.[35][36][37] 이렇게 하여 발생하는 돌연변이는 유전자의 기능이나 생성물에 영향을 줄 수 있다. 초파리를 이용한 돌연변이 연구의 결과 돌연변이의 약 70%는 개체에게 해로운 형태로 발현되었다.[38] 이러한 해로운 돌연변이가 개체의 세포 단위에서 발생한 경우 개체는 DNA 수리를 통해 돌연변이를 제거하도록 진화되었다.[35] 이를 통해 생물 개체는 물질대사의 과정에서 세포단위의 돌연변이를 억제하여 과도한 돌연변이의 발생에 따른 위험을 회피할 수 있다.[39] 한편, 레트로바이러스와 같은 몇몇 종은 돌연변이 발생 비율이 높아 몇 세대 지나지 않아 다양한 돌연변이를 갖는 자식 세대가 등장한다.[40] 이러한 높은 돌연변이 발생률은 인간의 면역계를 회피할 수 있어 바이러스의 생존에 유리하게 작용한다.[41]
돌연변이의 대표적인 사례로는 유전자 중복이 있다. 동물의 경우 매 천 년당 한 번 꼴로 발생하는 유전자 중복은 염색체의 일정 구간이 실수로 반복하여 복제되는 것이다.[42] 대부분의 유전자들은 상동성을 갖는 유전자족에 자리잡고 있다.[43] 원본 DNA를 복제하는 과정에서 발생하는 유전자 중복은 상동성을 깨뜨리고 유전자가 다른 기능을 하도록 만들 수 있다.[44][45] 즉, 유전자 중복에 의해 새롭게 형성된 DNA 염기서열은 단백질 도메인의 순서를 바꾸고 이 결과 원본 DNA와는 다른 단백질을 형성하게 한다.[46] 이해를 돕기 위해 인간의 눈을 예로 들면 망막에는 세 종류의 원추 세포와 간상 세포가 있어 빛을 감지 한다. 세 종류의 원추세포는 각각 고유한 주파수 대역의 가시광선에 반응하여 색을 볼 수 있게 한다. 원추 세포를 형성하게 하는 유전자 중의 하나가 유전자 중복으로 이상을 일으키면 해당하는 원추세포가 정상적인 기능을 할 수 없게 되고 색각 이상이 발생할 수 있다.[47][48]
대부분의 돌연변이가 개체에게 해롭게 작용하기 때문에 결과적으로 진화의 과정에서 도태된다. 그러나 개체에게 유리한 돌연변이가 일어난다면 자연선택에 의해 보다 많은 자식에게 이 유전형질을 남기게 된다. 이러한 결과가 누적되어 진화가 진행된다.[49]
생식과 유전자 재조합[편집]

|

|
유성생식을 하는 양성 생물의 경우 자식 세대의 유전자는 양 부모의 유전자가 혼합된 형태로 형성된다. 유성생식의 과정에서 양쪽 부모에게서 물려받은 유전자는 서로 쌍을 이루는 염색체의 결합과정에서 재조합된다. 이러한 유전자 재조합을 거쳐 자식에게 전달된 유전형질은 독립의 법칙에 따라 독립적으로 유전된다.[50] 유전자 재조합과 재배열의 결과 대립형질이 변화하게 된다. 대립형질의 어느 한 쪽이 변한다고 해서 대립형질의 발현 빈도가 변화되는 것은 아니지만 대립형질의 유전적 특성 자체가 변화될 수 있다.[51] 유성생식은 다양한 개체차가 나타나게 하여 진화를 촉진하는 요소이다.[52][53] 양성 생식을 하는 생물에서 각기 다른 기능을 갖는 대립형질의 유전자가 짝을 이루는 염색체의 한 쪽씩 위치할 경우 각각의 대립형질이 분기되어 유전한다. 예를 들어 오른쪽 그림의 나방의 경우 짝을 이루는 염색체 A1-A2가 있을 때 흰색이 발현되게 하는 유전자 a1이 염색체 A1에 있고 이와 대립형질의 관계에 있는 검은색 유전자 a2가 염색체 A2에 있다면, 이 둘 모두를 갖고 있는 개체가 생식을 위해 감수 분열을 할 때에는 유전자 a1과 a2가 분리되어 독립적으로 유전하게 된다.[54] 이 때문에 유성생식을 하는 생물은 무성생식을 하는 생물에 비해 보다 환경에 적응할 수 있는 이점이 있다. 즉 환경이 변화하면 적응에 더 유리한 유전형질의 발현이 더 늘어나지만 염색체에는 발현되지 않은 대립형질도 여전히 독립적으로 유전되어 환경이 또 다시 변할 때 종을 지속할 수 있는 기회를 늘리게 된다.[55]
동일한 염색체에 대립형질이 존재할 때에는 유전자 재조합 과정에서 분리되지 않고 함께 혼합되는 경우가 발생한다. 이와 같이 독립의 법칙을 따르지 않는 경우를 유전자 연관이라 한다. 두 유전자의 위치가 가까울 경우 거의 언제나 나뉘지 않고 함께 유전될 수 있는데 이를 단성체라 한다.[56]
무성생식과 비교할 때 유성생식이 갖는 이점을 제시하는 가설로 멀러의 깔쭉톱니 가설이 있다. 허먼 조지프 멀러는 무성생식을 하는 생물의 경우 유전자 재조합이 불가능하므로 한 번 일어난 돌연변이를 제거할 수 없기 때문에 불리한 돌연변이가 계속해서 누적되는 현상이 발생할 수 있다고 지적하였다. 한편, 유성생식의 경우에도 포유류의 Y 염색체와 같이 유전자 재조합이 불가능한 경우가 있다. 이러한 경우 유성생식 역시 멀러의 깔쭉톱니 가설에서 지적하는 불리한 돌연변이로 인한 피해가 발생할 수 있다.[57]
진화에 관한 또 다른 주요한 가설로는 붉은 여왕 가설이 있다. 이 가설의 주요 내용은 유성생식에 의한 진화의 속도에 비해 자연환경의 변화나 경쟁자의 진화 역시 계속해서 이루어지므로 어느 한 종이 다른 모든 경쟁자를 이기는 상황이 발생할 수 없다는 것이다.[58]
집단유전학[편집]
유전자의 관점에서 보면, 진화란 한 생물 종의 집단이 공유하고 있는 유전자 풀을 세대에서 세대로 물려주는 동안 그 안의 대립형질의 발현 빈도가 변화되는 것을 뜻한다.[59] 집단은 같은 생물 종 안에서 개별적인 그룹을 이루고 있다. 위에서 예를 든 나방의 경우, 대립형질인 색(흰색-검은색)의 발현 비율을 생각할 수 있다. 어느 숲에 있는 나방 집단이 처음에는 흰색이 많고 검은색이 적었다가 환경의 변화와 같은 이유로 검은색 나방의 발현이 점점 더 커져 어느 순간 대부분의 나방이 검은색이 되었다고 한다면 이 집단의 유전자 풀이 변화되었다고 할 수 있다. 진화는 이와 같은 유전자 풀 변화의 결과이다.
집단유전학에 따른 진화의 과정은 하디 와인버그 평형으로 설명될 수 있다. 충분히 큰 집단의 유전자 풀에서 대립형질의 발현 빈도가 오로지 유전자 재조합에 의해서만 일어날 때 그 집단의 대립형질 발현 빈도는 평형을 유지할 것이다. 그러나 현실 세계에서는 환경의 영향을 비롯한 수많은 요인이 대립형질의 발현 빈도를 조절하는 원인이 되기 때문에 장기적으로 보았을 때 유전자 풀의 변화는 필연적이다.[60]
유전자 이동[편집]

유전자 이동은 집단 사이에 유전자 교환이 이루어지는 것을 말한다. 일반적으로 같은 종 안에서 이루어진다.[62] 이동이나 육종, 꽃가루 교배 등에 의해 이루어지며 잡종이나 수평적 유전자 이동 등을 통해 이루어지기도 한다.
집단에 새로 들어온 개체는 그 집단의 유전자 풀의 변화를 가져오게 되고 대립형질의 발현 빈도를 변화시키게 된다. 이주는 유전자 풀을 변화시키는 주요한 원인이다. 한 때 같은 종이었다 하더라도 오랫동안 격리된 두 집단은 유전자 풀이 서로 다르게 변화하여 결국 종분화에 이르게 된다. 이러한 유전자 이동을 막는 지리적 격리의 원인으로는 산맥, 바다와 같은 지리적 요인 뿐 아니라 식물의 꽃가루 이동을 막는 만리장성과 같은 건축물도 포함될 수 있다.[63]
종분화가 이루어졌다 하더라도 최근 공통 조상으로부터 멀지 않다면 생식을 통해 잡종이 태어날 수 있다. 대표적인 예로 말과 당나귀의 잡종인 노새가 있다.[64] 이렇게 하여 태어난 잡종은 보통의 경우 생식 능력이 없는데 이는 염색체의 쌍이 일치하지 않아 감수분열을 할 수 없기 때문이다. 이 점은 두 개체가 같은 종인지 아닌지를 구별하는 방법으로도 사용된다. 잡종은 부모 양 쪽 종의 특징이 섞인 모습이 될 수도 있고 전혀 다른 모습을 지닐 수도 있다.[65] 두 부모 종과 최근 공통 조상이 유전자 차이가 아주 작을 경우 이들 사이에 생긴 잡종 역시 생식능력을 가질 수 있다. 자연에서 이런 경우가 흔하지는 않지만 네발나비과의 얼룩말나비 등에서 일어난 사례가 보고되어 있다.[66] 이 경우 잡종은 새로운 종이 된다. 이러한 잡종 종분화가 종분화 전체에 미치는 영향이 어느 정도인지는 밝혀지지 않았다.[65] 이와 관련하여 회색 나무 개구리를 이용한 실험이 활발히 이루어지고 있다.[67]
식물의 잡종에서는 두 배 이상의 염색체를 갖는 배수체와 같은 방식의 잡종 생식이 이루어질 수 있어 동물의 경우 보다 잡종 종분화가 쉽게 이루어질 수 있다.[68][69] 배수체는 감수분열의 과정에서 양 부모에게서 온 각각의 염색체가 별도로 분열할 수 있기 때문에 아주 작은 집단에서 일어날 수 있는 근친교배를 억제하는 방법이 될 수 있다.[70]
수평적 유전자 이동은 박테리아와 같은 종에서 일어나는 유전자 이동으로 한 개체에서 다른 개체로 유전 물질이 직접 이동되는 것이다.[71] 박테리아에서 일어나는 이러한 방식의 유전형질 전달로 인해 전혀 다른 종의 박테리아에게 항생제 내성이 전달될 수 있다.[72] 또한 박테리아는 도메인이 다른 경우에 조차 DNA를 전달할 수 있다.[73] 진화의 과정에서 진핵생물과 원핵생물은 큰 규모의 수평적 유전자 이동이 있었다. 대표적인 것으로는 진핵생물의 세포 소기관이 된 엽록체와 미토콘드리아가 있다.[74]
진화 메커니즘[편집]
진화가 이루어지는 중요한 두 원인은 자연선택과 유전자 부동이다. 자연선택은 환경에 적응하기 유리한 유전자가 다음 세대에게 전달될 확률이 높다는 것으로 그 결과 환경에 적응할 수 있는 유전형질이 진화에 반영된다. 유전자 부동성은 유전자 재조합의 과정에서 일어나는 무작위적인 변동으로 인해 대립형질이 발현될 가능성 역시 무작위적이라는 것이다. 이 두 요소와 함께 번식 가능한 크기를 갖는 집단에 자연 환경의 변화와 같은 요인이 작용하여 진화가 이루어진다.[75]
자연선택[편집]

자연선택은 세대 재생산의 과정에서 일어난 돌연변이가 여러 세대에 걸쳐 지속되게 하는 진화의 요인이다. 자연선택은 다음의 세가지 사항에 의해 일어나며 종종 "자기 증명" 작동 기제라고 불린다.
- 생물 집단 안에는 유전되는 개체차가 존재한다.
- 생물은 더 많은 자손을 번식하여 생존한다.
- 이러한 번식은 생물의 생존과 재생산의 가능성을 바꾼다.
위와 같은 조건에 따라 생물은 생존과 재생산을 위해 경쟁한다. 이러한 경쟁에 유리한 유전형질을 갖는 개체는 생존과 재생산에 성공하여 다음 세대에 유전형질을 물려줄 수 있으며 불리한 유전형질을 갖는 개체는 도태되어 다음 세대에 유전형질이 전달되지 못한다.[76]
진화 과정에서 일어난 자연선택의 지표로 한 생명체의 적응도를 고려할 수 있다. 적응도는 생물 집단에서 특정한 독립적인 유전형질을 가진 이전 세대의 개체 수에 대한 다음 세대의 개체 수를 비율로 나타낸 것이다. 적응도가 높다면 자연선택의 결과 이 유전형질이 고착되어 진화에 영향을 주게 된다. 적응도가 낮다면 해당하는 유전형질이 유전되지 못하게 된다.[77]
집단 내에서 대립형질 가운데 하나의 적응도가 점차 높아지는 것은 다른 대립형질들의 수가 줄어드는 것을 의미한다. 이러한 현상이 계속되면 결국 적응도가 높아진 대립형질이 그 종의 대표적 특징이 된다. 하나의 유전형질이 갖는 적응도는 고정적인 것이 아니다. 환경이 변하여 유전형질이 갖는 이득이 사라진다면 적응도는 변화할 것이다.[78]

집단 내에서 일어나는 자연선택은 그 방식에 따라 세가지로 나뉠 수 있다. 첫 번째 방식은 지향성 선택으로 한 생물 집단에 지속적으로 작용하는 동일한 환경 요인 등에 의해 한 방향으로 이루어지는 진화이다. 진화가 진행되는 동안 서서히 키가 커지는 생물집단이 이러한 직접 선택의 사례이다.[79] 두 번째 방식은 분열성 선택으로 한 생물 집단이 갖는 특정한 유전형질이 진화를 거치면서 뚜렷이 나뉘는 경우이다. 앞서 말한 키의 경우 작은 키 집단과 큰 키 집단으로 나뉘어 이전의 중간 키 집단은 사라지는 경우가 이에 해당한다. 마지막의 경우는 안정성 선택으로 집단의 대표적인 유전형질의 적응도가 보다 증가하는 경우이다. 즉, 키의 경우 평균적인 개체수가 증가하고 작거나 큰 개체수는 줄어들게 된다.[80]
짝짓기와 관련된 유전형질의 선택을 성선택이라 한다. 짝짓기 상대의 주의를 끌 수 있는 유전형질은 그렇지 못한 것보다 자손을 많이 남기게 되고 이러한 선택이 반복되면 결국 그 생물 집단의 대표적 특성이 된다.[81] 여러 종류의 생물 종에서 나타나는 수컷의 화려한 색이나 큰 뿔 등은 이러한 성 선택의 결과이다. 이러한 유전형질은 심지어 수컷의 생존에 불리할 정도로 과도하게 발달하는 경우도 있다.[82] 이스라엘의 생물학자 아모츠 자하비는 성 선택의 요인에 대해 게임 이론을 도입한 핸디캡 가설을 주장하였다.[83]
결국 자연선택이란 생물 집단 내에 있는 개체가 맞닥뜨리는 자연 환경의 여러 요인에 대해 얼마나 적응할 수 있는지를 나타내는 말이다.
유전자 부동[편집]

유전적 부동은 한 세대에서 다음 세대로 전달되는 대립형질의 발현빈도의 변화를 뜻한다. 개체에게 전달되는 유전자는 부모 유전자의 무작위적 표집이기 때문에 서로 다른 조합들을 물려받은 자식 세대의 개체들은 놓여진 환경에서 생존과 재생산을 할 수 있는 기회를 갖게 된다. 수학의 관점에서 보면 대립형질의 발현은 표본 오차와 관련되어 있다. 결과적으로 대립유전자 빈도는 무작위 행보를 보인다. 환경 요인에 의한 자연선택은 이러한 무작위 행보의 방향에 영향을 미친다. 즉, 생존과 재생산에 유리한 유전형질은 점차 상향되며 불리한 유전형질은 하향하게 된다. 이 과정이 지속되면 결국 집단 내에서 특정한 유전형질이 사라지거나 대표적인 특성이 되는 고착이 일어나게 된다. 때문에 동일한 유전자를 갖고 있었던 집단이라 할지라도 유전적으로 격리되어 서로 다른 환경에 놓이게 되면 유전적 부동의 진행이 달라질 수 있다. 두 집단에서 대립형질의 발현빈도가 서로 다르게 나타나는 것이 오랫동안 지속된다면 결국 두 집단은 서로 다른 유전자 대립형질 세트를 갖게 될 것이다.[84]
대립형질이 고착되는 시기가 언제 일 것인지는 집단의 규모와 관련이 있다. 집단의 규모가 작을 경우 고착은 급격히 진행된다.[85] 고착이 급격히 일어나는 집단 크기의 한계를 유효 집단 크기라 한다. 이때 유효 집단의 개체 수는 집단의 전체 개체 수 중에서 너무 어리거나 늙어서 짝짓기를 할 수 없는 개체를 제외한 개체 수만을 고려한다.[86]
현대의 진화 생물학은 자연선택과 유전적 부동이 조합된 결과, 진화가 일어난다고 파악한다.[87] 중립 진화 이론에서는 진화의 주된 요인을 유전적 부동에서 찾는다. 즉 진화의 대부분이 환경 요인에 대해 중립적인 돌연변이가 유전적 부동에 의해 고착된 결과라고 파악하고 있다.[88] 이 이론은 많은 생물학적 증거에 의해 뒷받침되고 있다.[89] 한편, 중립 진화 이론에 보다 세세한 진화의 작동 기제를 보충한 이론은 유사 중립 진화 이론이라 불린다. 이 이론의 주요 내용은 대부분의 돌연변이가 적응도에 주는 영향이 크지 않다는 것이다.[76]
이와 같이 유전자 부동을 진화의 주요 원인으로 고려할 때 한 생물집단의 규모가 갑자기 줄어들 경우 기존의 방향과는 전혀 다른 방향으로 유전형질의 고착이 일어날 수 있다. 그 생물 집단이 원래 가지고 있던 크기에 비해 아주 작은 개체수만이 살아남을 경우 표본 오차의 정도가 커지게 되고, 거기에 더해 집단의 크기가 줄어들면 고착이 급격히 진행되기 때문이다. 이와 같이 집단의 크기가 갑자기 줄어들어 진화에 영향을 주게 되는 현상을 유전자 병목 현상이라 한다. 자연 상태에서 생물 집단은 여러 가지 이유에서 이러한 유전자 병목 현상을 겪게 된다. 1890년대 사냥으로 인해 멕시코만에 있는 바다코끼리의 한 개체군이 약 20마리로 줄어들었다. 이 종의 경우 몇 마리의 수컷이 전체 암컷과 교미를 하므로 실제 교배 개체수는 더욱 적었을 수도 있다. 연구 결과 이 바다코끼리의 24개 단백질에서 개체차는 거의 나타나지 않았다. 반면 이 보다 남쪽에 살던 다른 바다코끼리 개체군에서는 훨씬 다양한 유전자 부동이 관찰되었다. 현재 이 바다코끼리 집단은 빠르게 그 수가 회복되고 있어 이러한 유전자 병목 현상이 생존에 위협이 되지는 않았던 것으로 보인다. 그러나 연구자들은 동일한 이 집단이 유전자 다양성 감소로 인해 질병이나 그 밖의 환경 요인에 취약할 수 있음을 우려하고 있다.[90]
결과[편집]
진화는 모든 생물에게 일어나고 있다. 현재의 생물 개체들은 자연선택에 대한 적응의 결과이다. 이러한 적응은 먹이를 찾고 포식자를 피하는데 유리한 몸의 형태 등과 같이 생물 개체가 살아가는 데 유리하도록 고착된 유전형질의 결과물이다. 생물들은 이러한 적응의 과정에서 공생과 같이 서로 협력하기도 한다. 오랜 기간 동안 이루어진 분열성 선택의 결과 하나의 종이 서로 교배될 수 없는 다른 종으로 분화되기도 한다.
멸종이나 종분화와 같이 종 전체에서 일어나는 진화의 과정을 대규모 진화라 한다. 이에 비해 같은 종에 속하는 특정 집단에서만 일어나는 적응과 같은 진화는 소규모 진화라 한다.[91] 일반적으로 대규모 진화는 오랜 기간 동안 이루어진 소규모 진화의 결과이다.[92] 대규모 진화와 소규모 진화는 한 가지 기준으로 쉽게 구별할 수 있는 것이 아니지만 단순화하면 대규모 진화가 보다 오랜 기간에 걸쳐 일어나는 것이라 할 수 있다.[93] 소규모 진화에서는 종 전체의 유전형질이 중요하다. 개체들 사이에 있는 유전형질의 차이들이 합하여져 급격한 적응과 새로운 행동 양식을 이끌고 불리한 유전형질을 지닌 개체는 도태된다. 이러한 현상을 보다 큰 지역을 놓고 보면 하나의 종 가운데 일부 집단이 격리될 경우 종분화의 진행이 보다 증가하게 된다. 이러한 관점에서 대규모 진화와 소규모 진화를 비교하면 소규모 진화는 개체와 유전자 수준에서 일어나는 현상이고 대규모 진화는 종 전체에서 일어나는 종분화 및 멸종의 과정이라 할 수 있다.[94][95]
진화에 대한 일반적인 오해 가운데 한 가지는 진화에 어떤 장구한 계획이나 목적이 있을 것이라 믿는 것이다. 그러나 실제 일어나는 진화에는 장구한 목적이 있지 않으며 보다 복잡함을 추구하는 계획 같은 것 역시 불필요하다.[96][97] 진화의 결과 나타나는 진화의 복잡성 증가는 전체 생물체의 수가 증가하면서 나타나는 부수적인 효과일 뿐이며, 단순한 형태의 생물은 그대로 유지되는 것이 보다 일반적이다.[98] 단적인 예로 전체 바이오매스의 절반을 차지하는 원핵생물들이 여전히 작은 크기를 유지하고 있는 사실을 들 수 있다.[99] 또한 이들 원핵생물들은 지구에서 나타난 생물 다양성의 압도적 다수를 차지한다.[100] 지구 전체의 역사를 통틀어 생물의 일반적인 형태는 단세포 생물이며 오늘날에도 이러한 사실에 변함이 없다. 보다 크고 복잡한 생물들이 주목 받는 까닭은 그것이 눈에 띄기 쉽기 때문이다. 이는 관찰자가 표본을 선택할 때 일으키는 편향 표본의 수집인 것이다.[101] 미생물은 진화의 속도가 급격하여 진화의 결과를 실시간으로 관찰할 수 있기 때문에 실험진화학의 중요한 관찰대상이다. 이 때문에 오늘날에는 미생물의 진화에 대한 연구가 점차 중요하게 다루어지고 있다.[102][103]
적응[편집]
적응은 생물학의 기본적 현상으로[104] 생물이 자신의 서식지에 보다 알맞은 형태로 변화하는 과정이다.[105] 또한 유전형질의 변화에 의한 적응은 생물 종의 생존에 중요한 요건이 된다. 말을 예로 든다면 말의 이빨은 풀을 뜯기에 알맞은 형태로 적응되었으며 다리는 포식자로부터 빠르게 도망칠 수 있도록 적응되었다. 적응은 유전형질이 변화해 가는 과정을 가리키는 개념이고 그 결과 나타난 생물의 특성은 적응형질이라 한다. 적응의 과정은 자연선택에 의해 이루어진다.[106] 테오도시우스 도브잔스키는 이를 다음과 같이 정리하였다.
- 1. 적응은 생물이 서식지에서 보다 잘 살 수 있도록 하는 진화의 과정이다.[107]
- 2. 적응도는 생물이 주어진 서식지에 얼마나 적합하게 진화되었는지를 나타내는 것으로 생물의 생존 정도와 재생산 정도로 나타낼 수 있다.[108]
- 3. 적응형질은 생물이 생존하고 재생산하는데 유리한 방향으로 진행된 유전형질의 발현 특징이다.[109]
적응은 이로운 특징의 발현은 촉진되고 불리한 특징의 발현은 줄어들면서 이루어진다. 박테리아가 항생물질에 적응하여 진화하는 것을 예로 들 수 있다. 박테리아는 약물이 개체에 주는 영향력을 감소시키고 약물 자체를 체외로 내보낼 수 있는 구조로 변화하여 결국 항생제 내성이 생기게 된다.[110] 보다 극단적인 사례들도 있다. 대장균 장기 진화 실험에서 대장균은 시트르산을 양분으로 사용할 수 있었다.[111] 심지어 플라보박테리움은 나일론을 양분으로 변화시키는 효소를 만들어 내었다.[112][113] 토양 박테리아의 일종인 스핑고비움은 농약으로 사용된 펜타클로로페놀의 독성을 약화시키기는 새로운 대사회로를 갖는 형태로 적응하였다.[114][115] 여전히 논란이 있으나 유전자 다양성을 발현시키는 생물의 능력이 적응의 성공과 밀접한 관련이 있다는 이론이 점차 지지를 얻어가고 있다. 얼마나 성공적으로 적응할 수 있는지를 나타내는 척도로 진화도란 개념이 제시되었다.[116][117]
위와 같은 극적인 사례가 있는 반면 대부분의 적응은 굴절적응에 의해 이루어진다. 굴절적응은 원래 다른 기능을 갖고 있던 생물의 일부분이 또 다른 기능에도 사용되면서 나타나는 적응형질이다. 이러한 사례로는 아프리카 도마뱀인 Holaspis guentheri에서 발견할 수 있는데 이 도마뱀은 갈라진 틈을 비집고 들어가기에 알맞은 납작한 머리를 가졌다. 또한, 이 도마뱀은 납작한 머리 덕분에 나무와 나무 사이를 활공하여 옮겨 다닐 수 있다.[118] 굴절적응의 또 다른 사례로는 동물의 눈에 있는 수정체 사이에서 형성되는 수용성 단백질인 크리스탈린의 형성 과정에 해당 작용과 이물질 대사가 관여하는 것을 들 수 있다.[119][120]


적응으로 인한 진화가 지속적으로 일어난 경우 같은 류의 생물의 상동성을 갖는 기관이 매우 다양한 형태로 분화된다. 이러한 상동 기관의 예로는 박쥐의 날개와 인간의 손, 고래의 지느러미가 같은 뼈 구조로 되어있다는 점을 들 수 있다. 이들 모두에서 뼈는 마디가 달린 다섯 가닥의 구조로 되어있다. 대왕판다의 "가짜 엄지"는 손목의 종자뼈에서 진화된 것이다. 이는 생물의 적응이 무궁무진할 수 있다는 사실을 보여준다.[121]
적응의 과정에서 어떠한 기능은 새로운 환경에 불리할 수 있다. 이렇게 불리해진 기능은 점차 발현이 억제되는 방향으로 적응이 진행되어 흔적만이 남게 되기도 한다. 이러한 기관을 흔적 기관이라 한다.[122] 흔적 기관의 사례로는 동굴 속에 사는 물고기가 시각 기능이 없는 눈을 달고 있는 경우[123], 날지 못하는 새에 남아있는 날개[124], 고래나 뱀에 남아있는 엉치뼈[125] 등이 있다. 인간의 경우에도 이러한 흔적기관들이 있는데, 한 때 초식 동물이었음을 보여주는 사랑니[126], 여전히 남아있는 꼬리뼈와 충수[122] 등이 그것이다. 유전자 단위에서도 이러한 흔적들이 남아 있게 되는데 이를 슈도진이라 한다. 슈도진은 예전에는 유의미한 기능을 하는 유전자였으나 돌연변이로 인해 그 기능이 상실된 유전자들이다. 생물의 게놈에는 이러한 슈도진이 상당한 부분을 차지하고 있는 경우가 흔하다.[127]
생태학에서 많은 지지를 받고 있는 가설인 경쟁 회피 가설에 따르면 같은 생태적 지위와 같은 환경을 놓고 경쟁하는 두 종이 오랫동안 공존할 수는 없다.[128] 때문에 자연선택의 압력이 가해지면 두 종은 서로 다른 생태적 지위를 갖도록 적응된다. 이 가설은 시클리드 물고기가 서식지에 따라 다양한 종분화를 이루어 서로 다른 먹이를 택하게 된 사실을 설명해준다.[129]
현대의 진화 발생 생물학은 발생을 적응과 굴절적응의 결과로서 파악한다.[130] 이 연구에서는 배발생의 과정에서 이루어지는 발생의 변형과 그것의 진화적 기원을 다룬다.[131] 진화 발생 생물학의 연구 사례로는 포유류의 턱 골격 형성과 중이의 형성 관계와 같은 것이 있다.[132] 또 다른 연구 분야로는 닭의 부리 발생과 악어의 이 발생에 관여하는 유전적 차이에 대한 연구와 같은 것이 있다.[133] 오늘날의 연구 결과, 이러한 차이는 해당 유전자 사이에 존재하는 아주 작은 차이 때문인 것으로 밝혀졌다.[134]
현대에는 CRIPR/Cas기술을 이용해, 손의 진화과정을 밝혀내기도 했다.[135]
공진화[편집]
 캘리포니아영원 |
 해안누룩뱀 |
생물들 사이에서는 경쟁과 협력 같은 상호작용이 끊임없이 이루어진다. 병원체와 숙주, 먹이사슬의 포식자와 같은 관계에서 이루어지는 이러한 상호 관계는 결과적으로 진화의 요인이 된다. 하나의 종이 다른 종과의 상호작용 결과 진화한다면 그에 영향을 준 다른 종 역시 진화하게 된다. 이와 같이 생물체간 상호작용의 결과 일어나는 진화를 공진화라 한다.[136] 공진화의 예로는 맹독인 테트로도톡신을 만드는 도롱룡 캘리포니아영원(Taricha granulosa)과 이를 잡아먹는 해안누룩뱀(Thamnophis sirtalis)을 들 수 있다. 도롱룡이 포식자에 대항에 체내에 독을 만들게 되자 포식자는 이 독에 면역되는 진화를 해 온 것이다.[137]
공생[편집]
생물들 사이의 모든 상호작용이 경쟁적인 것만은 아니다.[138] 많은 상호관계가 서로에게 이득이 되는 방향으로 진화되어왔다. 단적인 예로 식물의 뿌리에 자라는 균근을 들 수 있다. 균근과 식물은 서로 영양분을 보다 효율적으로 흡수할 수 있도록 돕는다.[139] 균근은 식물의 뿌리 세포 안으로 들어와 살면서 당을 제공받는 대신 식물이 질소염을 흡수할 수 있도록 돕는다. 균근은 특정한 신호 전달을 통해 식물의 면역계가 균근을 죽이지 않도록 한다.[140]
같은 종끼리 군집을 이루는 것 역시 협력적인 진화의 결과이다. 꿀벌, 개미, 흰개미와 같은 진사회성 곤충은 군집 생활을 통해 서로를 보호하고 먹이를 공유한다. 동물의 몸을 이루는 체세포에서도 이와 같은 일이 이루어지고 있다. 체세포들을 유지하는데 관여되는 배세포가 좋은 예가 될 것이다. 체세포는 분열, 성장, 유지, 죽음의 단계마다 독특한 신호를 내보낸다. 동물의 신체는 이 신호에 따라 적절히 반응하여 신체가 유지될 수 있도록 한다. 만약 이러한 신호를 무시하여 체세포에 이상이 생기면 암으로 변화하게 된다.[141]
자신과 혈연적으로 가까운 자식이나 가족을 돌보는 혈연선택 역시 공생적 진화의 결과라 할 수 있다.[142] 이와 유사한 개념으로 자신이 속한 무리의 개체들을 서로 돌보는 군집선택이 있다.[143]
종분화[편집]

종분화는 하나의 종이 둘 이상의 종으로 나뉘는 진화의 과정이다.[144] 진화생물학은 종을 분류나 형태로 파악하기 보다는 발현형질의 통계적 상태로 파악한다. 물론 이러한 관점은 아직까지 일반적으로 받아들여지는 종의 개념과는 다르다. 예를 들어 기존의 분류학에서 곰과를 다룰 때에는 곰과의 전형성을 기초로 하기 마련이다. 그러나 진화생물학은 곰과의 공통적인 유전자 풀에 나타나는 유전형질의 통계적 분포를 기초로 한다. 다른 매우 가까운 종들과 곰과를 구분하게 해주는 것은 이러한 유전자 풀이 갖고 있는 유전형질을 비교하는 것이다.[145] 물론, 원핵생물과 같은 생물들의 경우 이와 같은 종 분류가 명확하게 판가름되지 않아 여전히 논쟁이 벌어지고 있다. 종을 나누는 기준을 무엇으로 할 것인지를 놓고 벌이는 이러한 논쟁을 종 구분 문제라 한다. 생물학자들은 종에 대한 다양한 개념 가운데 자신의 연구에 알맞은 하나를 선택하여 사용하고는 한다.[146] 최근 활발하게 연구되고 있는 영역은 종 자체 보다는 같은 종 내에서 특정한 생태를 보이는 집단으로 생물체의 집단 내 또는 집단간 상호작용이 주된 연구 대상이다.
종분화는 자연 상태에서 그리고 실험실에서 오랜 기간 동안 관찰되어 왔다.[147] 유성생식을 하는 생물의 경우 종분화는 기본적으로 유전적으로 격리된 집단들 간의 유전자 다양성에서 기인한다. 종분화의 작동 기제는 다음의 네종류로 나누어 살펴볼 수 있다.[148]
- 이소적 종분화: 하나의 집단이 지리적으로 격리되어 둘 이상의 집단이 된 경우 오랜 세월 서로 다른 환경에 적응하여 진화한 결과 서로 다른 종이 된다. 이와 같은 종분화를 이소적 종분화라 한다. 대부분의 종분화는 이와 같은 이소적 종분화에 의해 진행된다. 서식지 파편화가 일어나 집단들이 격리된 경우에도 이소성 종분화와 같은 현상이 진행된다.[148]
- 이동적 종분화: 집단 가운데 일부가 서식처를 옮겨 새로운 환경에 적응하여 일어난 종분화를 이동적 종분화라 한다. 기존의 집단에 비해 극히 적은 개체수가 새로운 집단을 이루었을 경우 유전적 부동이 커져 대립형질의 고착이 급속화되는데 이를 창시자 효과라 한다. 이로 인하여 기존의 집단과는 판이하게 다른 유전형질을 갖는 집단으로 진화하게 된다.[149]
- 근소적 종분화: 급격한 환경의 변화로 자연선택의 압력이 매우 강력해지면 같은 장소에 있는 집단이라 할지라도 적응과정의 차이가 발생하여 서로 다른 집단으로 분화될 수 있다. 이를 근소적 종분화라 한다. 광산으로 인해 토양이 중금속으로 급속히 오염된 곳에서 이에 대한 내성이 생긴 향기풀( Anthoxanthum odoratum)의 발현이 대표적인 사례로 보고되었다.[150]
- 생리적 종분화: 두 집단의 특징에 큰 차이가 발생하여 더 이상 교배에 적합하지 않은 생리적 격리가 발생한 경우이다.[151] 생리적 격리는 접합전 격리와 접합후 격리로 나눌 수 있다. 접합 전 격리는 서로 다른 공간에 서식하여 만나지 못하거나 활동 시간대가 다른 경우, 생식기의 구조가 서로 다르게 변화하여 짝을 지을 수 없는 경우 화학적인 이유로 정자와 난자가 수정이 되지 않는 것과 같은 경우이다. 한편, 접합후 격리로는 잡종 접합자가 여러 이유로 성숙할 수 없는 경우, 노새와 같이 잡종이 불임인 경우, 잡종의 생존율이 극히 낮거나 잡종이 언제나 한쪽 성만을 갖고 태어나는 경우와 같은 것이 있다.[152]
종분화는 단속평형설의 유력한 증거로 다루어진다. 단속평형설은 일정 기간 종들의 상태가 안정적으로 유지되다 환경 변화 등의 사건이 발생했을 때 다양한 종으로 급격한 진화가 이루어졌다는 이론이며, 여기서 말하는 짧은 시간 역시 수백만년 이상이다.[153]
종분화 현상은 직접적으로 관찰되며, 이것은 진화를 증명된 이론을 넘어, 관찰 가능한 사실인 것을 증명해주는 것이다.[154]
멸종[편집]

멸종은 종 전체가 절멸하는 것이다. 멸종은 종분화와 함께 생물 진화의 일반적인 현상이다.[155] 지구상에 존재했던 수많은 종류의 동물과 식물이 멸종하였다.[156] 멸종은 어떠한 생물에게도 일어날 수 있는 현상인 것이다.[157] 생명의 역사에서는 수 차례의 대멸종 사태가 있어왔다. 새를 제외한 지구상의 모든 공룡이 멸종한 백악기 제3기의 K-T 대멸종은 널리 알려져 있다. 그러나 이전 시기에도 전 생물종의 96%가 멸종하였던 페름기 대멸종과 같은 대멸종 사태가 있었다.[158]
수 천년 전부터 나타난 인류의 급격한 증가에 의해 시작된 생물의 대멸종은 현생 지질연대인 홀로세의 이름을 붙여 홀로세 대멸종이라 하기도 한다. 오늘날 대멸종의 비율은 홀로세 대멸종이 시작되기 전인 수 천년 전과 비교하였을 때 100내지 1,000배 정도 증가되어 있다. 이러한 추세대로 진행된다면 21세기 중반 무렵에는 전체 생물 종의 30% 정도가 멸종에 이를 것으로 추측된다.[159] 오늘날 생물 종 멸종의 가장 큰 원인은 인간의 활동이다.[160] 지구 온난화는 이러한 멸종을 가속시키는 원인으로 지목되고 있다.[161]
진화에서 차지하는 멸종의 역할은 아직 분명하게 밝혀지지 않았으며 특정 사안별로 연구가 진행 중이다.[158] 대멸종이 아닌 작은 규모의 멸종 사태는 종 사이에서 한정된 자원을 놓고 벌어진 경쟁의 결과일 수 있다. 이를 경쟁적 배타라 한다.[10] 즉, 하나의 종이 경쟁관계에 있는 상대 종을 절멸시킨 경우가 이에 해당한다.[162] 대멸종 역시 진화에 커다란 영향을 미친다. 대멸종 이후 살아남은 종들은 빠르게 확산하여 방산적응과 같은 진화를 겪는다. 이 결과 다양한 종분화가 급격히 나타나게 된다.[163]
진화의 역사[편집]
생물이 지구에 언제 처음 생겨났는 지는 확실하지 않다. 그러나 적어도 30억 년 전에는 원핵생물이 등장하였다. 이후 최초 공통 조상에서 분화된 생물의 세 도메인, 즉 원핵생물, 진핵생물, 고균은 각자의 적응과정을 통해 무수히 많은 종으로 분화되어 오늘날까지 진화하고 있다. 특히 16억 년 전쯤 출현한 진핵생물을 바탕으로 진화한 다세포 생물은 여러 가지 식물들과 동물들로 진화하였다. 최근에 원핵생물과 진핵생물의 중간단계가 발견되기도 했다.[164]
생물의 기원[편집]
진화생물학은 생명의 기원을 다루는 학문이 아니며, 일반적으로 생화학으로 분류된 화학진화는 이름만 비슷할 뿐 진화에 포함되지 않는다. 그러므로 이곳에서는 화학진화에 대해 기술한다. 화학진화의 메인 질문은 최초의 생물은 어떻게 해서 나타나게 되었는가에 대한 설명일 것이다. 그러나 지금까지의 연구 결과만으로는 최초의 생물 발생 기원은 확실히 알려지지 않고 있다.[165] 오늘날의 과학적 합의는 단순한 화학반응들의 복합적 상호 작용에 의해 최초의 생물이 발생하였다는 것이지만, 어떻게 하여 그러한 발생이 일어나는지에 대해서는 확실히 알려진 바가 없다.[166] 현재까지는 최초 공통 조상 또는 최초의 유전자 풀의 구조와 형태에 대한 단편적인 고찰만이 이루어져 있다.[167] 현재 제시된 가설로는 RNA와 같은 분자 단위 물질의 자기복제나,[168] 단순 세포의 결집[169] 등이 있다.
공통 조상[편집]

지구상의 모든 생물은 최초 공통 조상 또는 최초의 동일한 유전자 풀에서 분화되었다.[170] 오늘날 생존해 있는 모든 종은 종분화와 멸종을 반복하며 일어난 진화의 결과이다.[171] 최초 공통 조상은 생명이라고 부를 수 있는 최소한의 특징들을 지니고 있었다. 첫째, 최초의 생물은 어디라 특정할 수는 없으나 상당한 크기 이상의 지역에 분포하였다. 둘째, 그것들은 단 하나의 형태가 아니라 유사성을 갖는 다양한 형태를 취하고 있었다. 셋째, 최초 공통 조상으로부터 전해진 유전형질이 무엇이었는지는 알 수 없으나 최소한 어느 시점을 지나면서 가계도와 같이 세대에서 세대로 유전형질이 전달되는 군집을 이루고 살았다.[172] 한편, 현대 진화 이론은 찰스 다윈이 제시하였던 계통도인 생명의 나무는 더 이상 받아들이지 않는다. 오늘날의 생물 계통도는 수평적 유전자 이동과 같은 종간의 상호 연관으로 보다 복잡하게 얽혀 있다.[173] 때문에 쿠닌 골도브스키와 같은 학자는 생명의 계통을 수형도의 개념으로 파악하는 기존의 "생명의 나무" 개념을 대체하여 네트워크의 개념으로 파악하는 "생명의 그물"을 새로운 계통도로 제시한다.[174]
과거의 생물들은 진화의 역사에 대한 기록으로 이해될 수 있다. 화석은 과거 생물의 형태적 특징과 해부학적 특징을 알 수 있게 해준다.[175] 고생물학은 과거 생물의 화석과 현생 생물의 해부학적 구조 등을 비교하여 둘 사이의 연관 관계를 연구한다. 그러나 이러한 화석 연구는 신체의 일부가 뼈나 껍질, 이와 같은 단단한 구조로 되어 있는 경우에는 유용하나 그렇지 못한 세균이나 고균의 연구에는 그다지 도움이 되지 못한다. 때문에 최근에는 공통 조상의 존재 증거로서 생화학적 유사성이 중요하게 여겨지고 있다. 예를 들면 모든 생물은 모두 같은 뉴클레오타이드와 아미노산으로 이루어져 있다.[176]
분자유전학의 발전으로 생물의 게놈에서 보다 많은 사항들을 알 수 있게 되었다. 특히 돌연변이의 발생 빈도를 관찰하여 두 종이 언제 공통 조상으로부터 분화되었는지를 추정하는 분자 시계의 발견이 그것이다.[177] 이를 통하여 인간과 침펜지가 비교적 최근에야 분화되었음을 확인할 수 있었다.[178]
생명의 진화[편집]
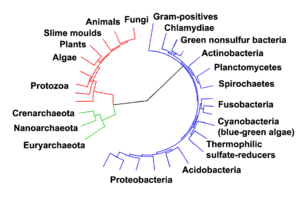
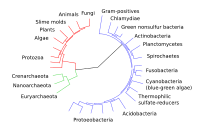
적색 - 진핵생물, 녹색 - 고균, 청색-세균
최초의 생물이 언제 출현하였는지는 정확히 알 수 없으나 30 ~ 40억 년 전 무렵 원핵생물이 출현하였다.[179] 이후 십수억 년 동안 생물의 형태는 계속해서 변화했다.[180] '살아 있는 분자들'은 더욱 발전하여 단세포 생물로 바닷속을 떠다녔다. 생명이 출현했다는 것을 보여 주는 가장 오래된 증거는 세균(박테리아)과 물에서 사는 식물의 화석이다. 이것들은 35억 년 된 암석에서 발견되었다. 이것을 시작으로 생물은 여러 방향으로 가지를 쳐 나갔다. 가장 큰 두 줄기는 식물과 동물이다.[181]
세포구조의 중대한 변화로 인해 진핵생물이 출현하였다. 내생공생자라 불리는 세포간 공생과정을 거쳐 미토콘드리아, 수소발생소포[182]와 같은 세포소기관의 형성이 진핵생물의 출현 요인으로 꼽히고 있다.[74][183] 한편 남조류와 같은 세균은 엽록체를 갖게 되었다.[184] 최초의 진핵생물 출현 시기는 정확치 않으나 16억 년 전 ~ 27억 년 전 무렵으로 추정된다.[179][185]
지금까지 발견된 가장 오래된 다세포 생물의 흔적은 6억 1천만 년경 살았던 것으로 추정되는 에디아카라 생물군이다. 여러 가지 형태의 다세포 생물이 독립적인 진화 과정을 거쳐 출현하였다. 최초로 등장한 다세포 동물은 해면동물, 갈조류, 남조류, 점균류, 점액세균과 같은 것들이었다.[186] 다세포 생물은 급격한 진화의 과정을 거쳤고 1억 년이 흐른 캄브리아기에 이르러 생물 다양성이 폭발적으로 증가하였다. 이를 캄브리아기의 대폭발이라 한다. 이때 이미 현생 생물의 형태와 관련이 깊은 대부분의 생물들이 출현하였다.[187] 이 시기의 급격한 생물 다양성의 증가는 광합성의 결과 대기권의 산소 농도가 증가하였기 때문이라 추정된다.[188] 5억 년 전 무렵이 되자 식물과 균계 생물이 지구 전역을 뒤덮게 되었으며 절지동물과 여러 동물들 역시 출현하게 되었다.[189] 3억 년 전 무렵 다른 양막류 동물들을 뒤따라 양서류가 등장하였다. 포유류의 출현은 2억 년 전 무렵에 일어났다. 1억 년 전 무렵에는 조류가 파충류에서 분화하였다. 이 모든 진화는 진핵생물의 출현에서 비롯된 것으로 성공적인 적응의 결과 지구 전체의 생물량에서 다수를 점유하게 되었다.[190]
일반적으로 생명의 진화에 걸리는 시간은 길며, 다수의 세대를 필요로 하나, Rapid Evolution, 즉 고속진화의 발견으로, 특정 환경에서 빠르게 일어나는 진화가 관찰된다는 점이 밝혀졌으며, 이는, 점진주의와 단속 평형론이 조화를 이룬 현대 종합적 진화학을 지지한다.
진화 이론의 역사[편집]
|
기원전 6세기 무렵 고대 그리스의 철학자 아낙시만드로스는 모든 생물이 최초 공통 조상에서 출발해 종분화를 거쳐 서로 다른 생물이 되었다는 진화의 개념을 제기했다.[192] 이와 같은 사고를 지지한 학자로는 그리스의 엠페도클레스, 고대 로마의 루크레티우스, 그리고 아랍 생물학자인 알 자히즈[193], 초기 이슬람 철학자인 이븐 미스카와이, 이콴 알 사파[194], 중국의 철학자 장자[195] 등이 있다.
18세기 무렵 생물학에 대한 이해가 깊어지면서 1745년 피에르루이 모페르튀가 진화론을 다시 과학의 범주로 끌어들였고 1796년 에라스무스 다윈이 재차 진화론을 주창하였다.[196] 당대에 가장 큰 영향을 준 진화 이론은 장바티스트 라마르크의 종의 변화에 대한 이론이었다. 찰스 다윈은 1838년부터 자연선택에 대한 자신의 이론을 체계화하기 시작하였다. 1858년 찰스 다윈은 런던 린네 협회의 알프레드 러셀 월리스와 공동으로 몇 개의 논문을 발표하여 자신의 진화 이론을 세상에 공표하였다.[197] 1859년 찰스 다윈의 《종의 기원》 초판이 출판되었다.
이후 벌어진 논쟁에서 찰스 다윈은 자연 선택의 결과 형성된 종들이 갖는 유전적 다양성을 갖게 되는 작동 기제를 논증하지 못했다. 찰스 다윈 역시 라마르크와 마찬가지로 종에 나타나는 새로운 특성은 개체가 살아있는 동안에 후천적으로 획득되는 것이라 생각했다.[198] 후천적인 형질이 유전될 수 있다는 진화이론을 용불용설이라 한다.[199] 1880년대에 이르러 아우구스트 바이스만은 후천적으로 획득된 형질이 유전되지 않는다는 것을 입증했다. 이로써 용불용설은 진화를 설명하는 데 부적합한 이론이 되었다.[200][201] 이런 와중에도 찰스 다윈은 유전형질을 세대에서 세대로 물려주는 작동기제가 무엇인지 여전히 설명하지 못하고 있었다. 1865년 그레고어 멘델은 어떠한 형질이 유전될 것인지를 미리 예측할 수 있다는 사실을 발견하였다.[202] 1890년대에 이르러 유전학과 생물통계학은 멘델의 유전법칙을 재발견하여 다윈의 진화 이론에 접목시켰다. 이로써 자연선택을 거친 유전형질이 다음 세대로 전달되는 작동 기제에 대한 설명이 가능해지는 중요한 계기가 되었다.
1890년대에 이르러 휘호 더프리스와 다른 초창기 유전학자들이 재발견한 멘델의 유전법칙은 당시에는 널리 알려지지 않은 이론이었으며 찰스 다윈과 월리스 역시 이 이론에 대해 접하지 못한 상태였다. 멘델의 유전법칙이 찰스 다윈의 진화 이론에 접목되어 "다양한 개체차를 일으키는 유전형질이 자연선택에 의해 선별되고 그 가운데 적응에 성공한 유전형질만이 자손에게 전달되어 진화가 이루어진다"는 현대 진화 이론의 기본적 토대가 확립되게 되었다. 이렇게 하여 정립된 진화 이론은 진화에 대한 다른 이론들을 제치고 가장 강력한 진화 이론으로 받아들여지게 되었다.[203]
1920년대에서부터 1930년대에 이르기까지의 기간 동안 홀데인, 슈얼 라이트, 그리고 로널드 피셔와 같은 진화생물학 학자들은 멘델의 유전법칙과 다윈의 진화이론을 보다 면밀히 연구하였다. 특히 로널드 피셔는 진화를 기본 개념으로 하는 집단유전학이라는 새로운 학문을 개척하였다. 이러한 연구의 결과 현대 진화 이론이 탄생하게 되었다.[204]
1940년대에 이르러 오스왈드 에이버리는 DNA에 대한 개념을 정립하였다. 1953년 제임스 D. 왓슨과 프랜시스 크릭은 DNA의 구조를 밝혀내었다. 이로써 유전학과 분자생물학이 진화생물학의 중요한 분야로 받아들여지게 되었다. 그 결과 계통학은 혁명적인 변화를 겪게 되었다. 초기의 진화생물학 연구자들은 주로 분류학의 전통 위에서 종의 진화를 관찰하고 연구하였다. 그러나 현대 진화 이론의 수립과 다양한 연구 분야의 확장으로 인해 오늘날의 진화생물학은 생물학 전반의 여러 분야와 밀접한 관련을 맺고 있다.[10]
스티븐 제이 굴드는 진화의 역사와 고생물에 대한 연구를 근거로 단속평형설을 제기하였다. 단속평형설은 종분화가 환경의 급격한 변화와 같은 특정한 이유가 발생할 때 급격히 이루어지며 그렇지 않을 때에는 오랜 기간 동안 종들이 유지된다는 이론이다. 리처드 도킨스는 진화의 결과 생물 집단이 얼마나 생존과 재생산에 성공하는가를 척도로 하는 진화도의 개념과 진화 과정에서 이루어지는 자연선택을 집단 단위로 파악하는 선택 단위의 개념을 제시하였다. 도킨스는 유전자와 진화의 관계를 놓고 스티븐 로즈와 논쟁을 벌이기도 하였다.[11]
오늘날 진화생물학과 관련이 깊은 학문으로는 생화학, 유전학, 생태학, 계통학과 같이 초창기에 이미 깊숙한 연관을 맺고 있던 학문에 덧붙여 심리학, 의학, 철학, 컴퓨터 과학과 같은 학문들이 추가되었다. 21세기에 들어서 진행되고 있는 현대의 진화 생물학 연구는 현대 진화 이론을 보다 넓게 확장시켜 선택 단위, 진화도와 같은 새로운 개념들과 후생진화생물학과 같은 새로운 학문 분야를 만들어 내었다.[205]
사회 문화적 반응[편집]
| 종교에 따른 진화 이론의 수용 정도 | |||||||||||
|
불교
81
|
힌두교
80
|
유대교
77
|
무종교
72
|
가톨릭교회
58
|
동방 정교회
54
|
주요 개신교
51
|
이슬람교
45
|
흑인 개신교
38
|
복음주의 개신교
24
|
몰몬교
22
|
여호와의 증인
8
|
| 출처:U.S.Religious Landscape Survey(2008년 6월)[206] 단위:%, 조사 대상: 미국인 | |||||||||||

1859년 찰스 다윈의 《종의 기원》이 출판된 이후 19세기 유럽은 격론에 휘말렸다. 진화 이론이 지니고 있는 종교적, 사회적 함의는 철학을 비롯한 여러 학회에서 뜨거운 논쟁거리였다.[207] 그러나 오늘날의 과학 문헌들은 생물의 진화를 자명한 것으로 다루며, 현대 진화 이론은 모든 과학 분야에서 폭넓게 수용되고 있다.[10] 그럼에도 일부 유신론자들에게 진화 이론은 여전히 논쟁의 대상이다.[208]
여러 종교들이 자신들의 신앙과 진화 이론을 조화시키려 한다. 유신진화론과 같은 것이 대표적이다. 유신진화론은 기존의 창조론과는 달리 자신들의 종교에 등장하는 창조 신화의 다양한 내용을 진화 이론의 입장에서 해석하고 있으며 신과 같은 해당 종교의 믿음의 대상이 "진화의 목적"을 갖고 있다고 믿는다. 미국의 개신교의 경우 대부분은 유신진화론을 수용하나 남침례교와 한국의 보수적 기독교 교단은 이를 인정하지 않는다.[209] 이 과정에서 수많은 유사과학이 발생하기도 한다. 또한 경전이 쓰여진 시대적 배경으로 인하여 현대과학과 맞지 않게 쓰여진 것일 뿐이므로 경전을 문자적으로 해석 할 필요가 없으며 경전의 맥락적 내용과 과학적 사실의 조화를 이룰 수 있다는 선아담인류론 등의 이론도 존재한다.
한편 19세기 허버트 스펜서에 의해 멜더스의 이론에서 출발한 사회진화론과 같은 사상은 자연선택의 원리를 사회에 부당하게 적용하여 적자생존을 주장하였다. 이 사상은 평등에 대한 불인정, 성 차별, 인종 차별, 제국주의와 같은 것을 정당화시키기 위해 사용되었다.[210] 그러나 사회진화론은 다윈의 주장과는 아무런 관련이 없는 이론이며, 더욱이 이 이론은 어떠한 과학적 방법에 의한 증거 자료도 제시하지 못하였다.[211][212]
적용[편집]

|

|
| 인류가 가장 먼저 기르기 시작한 가축의 하나인 개는 가축화의 과정에서 일어난 인위적 선택에 의해 다양한 집단으로 분화되었다. | |
자연선택에 의해 일어나는 진화의 과정을 설명하는 진화 이론은 다른 많은 과학분야에 적용되었다.[213] 진화 이론의 주요 적용 분야는 인위적 선택이 필수적인 육종학이다. 농업에 의해 재배되기 시작한 식물들과 가축화된 많은 동물들이 인간의 인위적 선택에 의해 특정 유전형질이 특화되었다.[214] 최근에는 분자생물학 수준에서 DNA 내의 항생제 내성 유전자와 같은 특정 선발 표지를 이용하여 유전자를 조작하는 유전공학을 통한 인위적 선택이 이루어지고 있기도 하다. 유전공학은 반복적 돌연변이의 유발과 기 결과 나타나는 특정 형질을 갖는 단백질을 선택함으로써 효소를 변형시키거나 새로운 항체를 형성하게 하는 등의 방법으로 생물의 유전형질을 변형시킨다. 이를 방향성 진화라 한다.[215]
생물 개체의 진화 과정에 대한 이해가 깊어지면서 신체의 형성과 유전자의 관계에 대한 지식 역시 보다 넓어졌다. 이를 통해 축적된 지식은 인간의 유전 질병 치료 등에 사용되고 있다.[216] 이와 관련된 사례로는 동굴에 서식하여 진화의 과정에서 시각이 사라지고 백변증이 나타난 멕시코 테트라를 이용한 연구가 있다. 이 실험에서는 서로 다른 동굴에 서식하는 멕시코 테트라를 교배하여 태어난 자식 세대들을 관찰하였다. 서로 다른 유전자 풀의 유전자 재배열 결과 이들의 돌연변이 중 일부는 다시 정상적인 시각이 있는 눈을 갖춘 개체들이 발현하였다.[217] 이 연구는 시각 기관의 색소 침착에 관여하는 유전자에 의해 진행되는 크리스탈린과 멜라토닌 1 수용기의 형성이 시각 기능에 밀접한 연관이 있음을 보여준다.[218] 또 다른 사례로는 남극암치아목과 제브라피쉬에 대한 연구가 있다. 남극암치아목은 적혈구를 거의 생성하지 않는 유전형질이 고착되어 있다. 이와 친족관계에 있는 제브라피쉬의 유전자는 남극암치아목이 보다 많은 조혈세포를 갖도록 할 수 있었다.[219]
진화가 보여주는 능률적인 과정과 네트워크는 컴퓨터 과학에도 많은 영향을 주었다. 1960년대에 노르웨이 출신의 이탈리아 수학자인 닐스 알 바리셀리는 진화 시뮬레이션을 사용한 진화 알고리즘(evolutionary algorithm)을 적용하여 제작한 인공 생명을 선보였다. 영국 출신의 컴퓨터 과학자 알렉스 프레이저는 이를 보다 확장하여 인공 생명에 대한 인위적 선택 시뮬레이션의 결과를 발표하였다.[220] 1960년대 말에서 1970년대 초 독일의 컴퓨터 과학자 잉고 레센베르그는 진화 전략을 수립하여 복잡한 공학적 문제를 해결하는 인위적 진화 작업을 수행하였다. 오늘날 레센베르그가 제안한 인위적 진화의 개념은 다양한 분야에서 활용되고 있다.[221] 미국의 컴퓨터 과학자 존 헨리 홀랜드에 의해 제시된 유전자 알고리즘[222] 은 컴퓨터 성능의 급격한 증가에 힘입어, 진화의 개념을 도입한 프로그램이 실용적인 문제를 해결하는데 이용될 수 있음을 보였다.[223] 오늘날 진화 알고리즘은, 특정한 문제의 영역에서, 다차원의 최적화 문제를 해결하는데 효율적으로 기여하고 있다.[224]
같이 보기[편집]
외부 링크[편집]
- 네이버 캐스트 - 성의 진화, 진화의 실험실, 병원, 진화의 현장, 눈먼 시계공, 진화의 도박, 유전적 부동, 돌연변이 맹신의 헛점, 공작새의 화려한 꼬리, 자연선택의 원리, 진화론, 그 간결미
- 진화 생물학 입문 (Introduction to Evolutionary Biology)
- (영어) Evolution 101
 위키인용집에 진화 관련 문서가 있습니다.
위키인용집에 진화 관련 문서가 있습니다.
각주[편집]
- ↑ Gould, S.J. (2002). The Structure of Evolutionary Theory. Cambridge: Belknap Press (Harvard University Press). ISBN 0-674-00613-5.
- ↑ Futuyma, Douglas J. (2005). 《Evolution》. Sunderland, Massachusetts: Sinauer Associates, Inc. isbn 0-87893-187-2.
- ↑ “The marbled crayfish as a paradigm for saltational speciation by autopolyploidy and parthenogenesis in animals.”.
- ↑ Lande R, Arnold SJ (1983). "The measurement of selection on correlated characters". Evolution 37: 1210–26. doi:10.2307/2408842
- ↑ Ayala FJ (2007). "Darwin's greatest discovery: design without designer Archived 2011년 10월 26일 - 웨이백 머신". Proc. Natl. Acad. Sci. U.S.A. 104 (Suppl 1): 8567–73. doi:10.1073/pnas.0701072104. PMID 17494753
- ↑ Ian C. Johnston (1999). "History of Science: Early Modern Geology Archived 2008년 7월 1일 - 웨이백 머신". Malaspina University-College. Retrieved 2008-01-15
- ↑ Darwin, Charles (1859). On the Origin of Species (1st ed.). London: John Murray. p. 1. . Related earlier ideas were acknowledged in Darwin, Charles (1861). On the Origin of Species (3rd ed.). London: John Murray. xiii.
- ↑ AAAS Council (December 26, 1922). "AAAS Resolution: Present Scientific Status of the Theory of Evolution Archived 2011년 7월 17일 - 웨이백 머신". American Association for the Advancement of Science.
- ↑ 로널드 L. 넘버스 (2016). 《창조론자들》. 새물결플러스. 48쪽. ISBN 9791186409558.
- ↑ 가 나 다 라 Kutschera U, Niklas K (2004). "The modern theory of biological evolution: an expanded synthesis". Naturwissenschaften 91 (6): 255–76. doi:10.1007/s00114-004-0515-y. PMID 15241603
- ↑ 가 나 다 각각의 이론에 대한 보다 자세한 정보는 아래의 참고 문헌을 볼 것
- ↑ “IAP STATEMENT ON THE TEACHING OF EVOLUTION” (PDF). the Interacademy Panel on International Issues. 2007년 9월 27일에 원본 문서 (PDF)에서 보존된 문서. 2007년 4월 25일에 확인함.
- ↑ “Statement on the Teaching of Evolution” (PDF). American Association for the Advancement of Science. 2006. 2007년 3월 20일에 확인함.
- ↑ “Rapid Evolution Changes Species in Real Time”. DISCOVERY. 2015년 5월 9일에 확인함.
- ↑ “Mechanistic Basis of Resistance to PCBs in Atlantic Tomcod from the Hudson River”. Science. 2015년 5월 9일에 확인함."Science 11 March 2011: Vol. 331 no. 6022 pp. 1322-1325 DOI: 10.1126/science.1197296
- ↑ “HAR1 mediates systemic regulation of symbiotic organ development”. Nature. 2015년 5월 9일에 확인함. "Nature 420, 426-429 (28 November 2002) | doi:10.1038/nature01231; Received 22 July 2002; Accepted 21 October 2002; Published online 6 November 2002"
- ↑ Sturm RA, Frudakis TN (2004). "Eye colour: portals into pigmentation genes and ancestry". Trends Genet. 20 (8): 327–32. doi:10.1016/j.tig.2004.06.010. PMID 15262401
- ↑ Pearson H (2006). "Genetics: what is a gene?". Nature 441 (7092): 398–401. doi:10.1038/441398a. PMID 16724031.
- ↑ Visscher PM, Hill WG, Wray NR (April 2008). "Heritability in the genomics era—concepts and misconceptions". Nat. Rev. Genet. 9 (4): 255–66. doi:10.1038/nrg2322. PMID 18319743
- ↑ Oetting WS, Brilliant MH, King RA (1996). "The clinical spectrum of albinism in humans". Molecular medicine today 2 (8): 330–5. doi:10.1016/1357-4310(96)81798-9. PMID 8796918
- ↑ Phillips PC (November 2008). "Epistasis—the essential role of gene interactions in the structure and evolution of genetic systems". Nat. Rev. Genet. 9 (11): 855–67. doi:10.1038/nrg2452. PMID 18852697.
- ↑ 가 나 Wu R, Lin M (2006). "Functional mapping - how to map and study the genetic architecture of dynamic complex traits". Nat. Rev. Genet. 7 (3): 229–37. doi:10.1038/nrg1804. PMID 16485021.
- ↑ Stanford Encyclopedia of Philosophy. Evolutionary Genetics. January 14, 2005. Accessed 2007-07-07.
- ↑ Shi-Yan Ng, Lin Lin, Boon Seng Soh, Lawrence W. Stanton Trends in Genetics Volume 29, Issue 8, August 2013, Pages 461–468
- ↑ Elisabeth J. Chapman & James C. Carrington nature review Genetics 8, 884-896 (November 2007) | doi:10.1038/nrg2179
- ↑ Anton Nekrutenko, Wen-Hsiung Li Trends in Genetics Volume 17, Issue 11, 1 November 2001, Pages 619–621
- ↑ Artemy Beniaminov, Eric Westhof, and Alain Krol RNA RNA. 2008 Jul; 14(7): 1270–1275.
- ↑ Jordan P. Amadio, Christopher A. Walsh Cell Volume 126, Issue 6, 22 September 2006, Pages 1033–1035
- ↑ Assaf Zemach, Daniel Zilberman Current Biology Volume 20, Issue 17, 14 September 2010, Pages R780–R785
- ↑ “보관된 사본” (PDF). 2016년 11월 9일에 원본 문서 (PDF)에서 보존된 문서. 2016년 12월 21일에 확인함.
- ↑ Harwood AJ (1998)., Factors affecting levels of genetic diversity in natural populations., Philos. Trans. R. Soc. Lond., B, Biol. Sci. 353 (1366): 177–86. doi:10.1098/rstb.1998.0200. PMID 9533122
- ↑ Draghi J, Turner P (2006). "DNA secretion and gene-level selection in bacteria". Microbiology (Reading, Engl.) 152 (Pt 9): 2683–8. PMID 16946263.
- Mallet J (2007). "Hybrid speciation". Nature 446 (7133): 279–83. doi:10.1038/nature05706. PMID 17361174.
- ↑ Butlin RK, Tregenza T (1998)., Levels of genetic polymorphism: marker loci versus quantitative traits., Philos. Trans. R. Soc. Lond., B, Biol. Sci. 353 (1366): 187–98. doi:10.1098/rstb.1998.0201. PMID 9533123.
- ↑ Wetterbom A, Sevov M, Cavelier L, Bergström TF (2006). "Comparative genomic analysis of human and chimpanzee indicates a key role for indels in primate evolution". J. Mol. Evol. 63 (5): 682–90. doi:10.1007/s00239-006-0045-7. PMID 17075697.
- ↑ 가 나 Bertram J (2000). "The molecular biology of cancer". Mol. Aspects Med. 21 (6): 167–223. doi:10.1016/S0098-2997(00)00007-8. PMID 11173079.
- ↑ Aminetzach YT, Macpherson JM, Petrov DA (2005). "Pesticide resistance via transposition-mediated adaptive gene truncation in Drosophila". Science 309 (5735): 764–7. doi:10.1126/science.1112699. PMID 16051794
- ↑ Burrus V, Waldor M (2004). "Shaping bacterial genomes with integrative and conjugative elements". Res. Microbiol. 155 (5): 376–86. doi:10.1016/j.resmic.2004.01.012. PMID 15207870.
- ↑ Sawyer SA, Parsch J, Zhang Z, Hartl DL (2007). "Prevalence of positive selection among nearly neutral amino acid replacements in Drosophila". Proc. Natl. Acad. Sci. U.S.A. 104 (16): 6504–10. doi:10.1073/pnas.0701572104. PMID 17409186
- ↑ Sniegowski P, Gerrish P, Johnson T, Shaver A (2000). "The evolution of mutation rates: separating causes from consequences". Bioessays 22 (12): 1057–66. doi:10.1002/1521-1878(200012)22:12<1057::AID-BIES3>3.0.CO;2-W. PMID 11084621
- ↑ Drake JW, Charlesworth B, Charlesworth D, Crow JF (01 April 1998). "Rates of spontaneous mutation". Genetics 148 (4): 1667–86. PMID 9560386
- ↑ Holland J, Spindler K, Horodyski F, Grabau E, Nichol S, VandePol S (1982). "Rapid evolution of RNA genomes". Science 215 (4540): 1577–85. doi:10.1126/science.7041255. PMID 7041255
- ↑ Carroll SB, Grenier J, Weatherbee SD (2005). From DNA to Diversity: Molecular Genetics and the Evolution of Animal Design. Second Edition. Oxford: Blackwell Publishing. ISBN 1-4051-1950-0
- ↑ Harrison P, Gerstein M (2002). "Studying genomes through the aeons: protein families, pseudogenes and proteome evolution". J Mol Biol 318 (5): 1155–74. doi:10.1016/S0022-2836(02)00109-2. PMID 12083509
- ↑ Orengo CA, Thornton JM (2005). "Protein families and their evolution-a structural perspective". Annu. Rev. Biochem. 74: 867–900. doi:10.1146/annurev.biochem.74.082803.133029. PMID 15954844
- ↑ Long M, Betrán E, Thornton K, Wang W (November 2003). "The origin of new genes: glimpses from the young and old". Nat. Rev. Genet. 4 (11): 865–75. doi:10.1038/nrg1204. PMID 14634634
- ↑ Wang M, Caetano-Anollés G (2009). "The evolutionary mechanics of domain organization in proteomes and the rise of modularity in the protein world". Structure 17 (1): 66–78. doi:10.1016/j.str.2008.11.008
- ↑ Gregory TR, Hebert PD (1999). "The modulation of DNA content: proximate causes and ultimate consequences". Genome Res. 9 (4): 317–24. PMID 10207154. http://genome.cshlp.org/content/9/4/317.full.
- ↑ Hurles M (July 2004). "Gene duplication: the genomic trade in spare parts". PLoS Biol. 2 (7): E206. doi:10.1371/journal.pbio.0020206. PMID 15252449.
- ↑ 말른 호아글랜드, 버트 도드슨, 황현숙 옮김, 생명의 파노라마, 사이언스북스, 2001, ISBN 89-8371-050-0
- ↑ Radding C (1982). "Homologous pairing and strand exchange in genetic recombination". Annu. Rev. Genet. 16: 405–37. doi:10.1146/annurev.ge.16.120182.002201. PMID 6297377
- ↑ Agrawal AF (2006). "Evolution of sex: why do organisms shuffle their genotypes?". Curr. Biol. 16 (17): R696. doi:10.1016/j.cub.2006.07.063. PMID 16950096
- ↑ Peters AD, Otto SP (2003). "Liberating genetic variance through sex". Bioessays 25 (6): 533–7. doi:10.1002/bies.10291. PMID 12766942
- ↑ Goddard MR, Godfray HC, Burt A (2005). "Sex increases the efficacy of natural selection in experimental yeast populations". Nature 434 (7033): 636–40. doi:10.1038/nature03405. PMID 15800622.
- ↑ Pouchkina-Stantcheva NN, McGee BM, Boschetti C, et al. (October 2007). "Functional divergence of former alleles in an ancient asexual invertebrate". Science 318 (5848): 268–71. doi:10.1126/science.1144363. PMID 17932297. Lay summary
- ↑ Fontaneto D, Herniou EA, Boschetti C, et al. (April 2007), Independently Evolving Species in Asexual Bdelloid Rotifers PLoS Biol. 5 (4): e87. doi:10.1371/journal.pbio.0050087. PMID 17373857. Lay summary.
- ↑ Lien S, Szyda J, Schechinger B, Rappold G, Arnheim N (February 2000). Evidence for Heterogeneity in Recombination in the Human Pseudoautosomal Region: High Resolution Analysis by Sperm Typing and Radiation-Hybrid Mapping Am. J. Hum. Genet. 66 (2): 557–66. doi:10.1086/302754. PMID 10677316
- ↑ Muller H (1964). "The relation of recombination to mutational advance". Mutat. Res. 106: 2–9. PMID 14195748
- ↑ Salathé M, Kouyos RD, Bonhoeffer S (August 2008). "The state of affairs in the kingdom of the Red Queen". Trends Ecol. Evol. (Amst.) 23 (8): 439–45. doi:10.1016/j.tree.2008.04.010. PMID 18597889
- ↑ Stoltzfus A (2006). "Mutationism and the dual causation of evolutionary change". Evol. Dev. 8 (3): 304–17. doi:10.1111/j.1525-142X.2006.00101.x. PMID 16686641
- ↑ O'Neil, Dennis (2008). "Hardy-Weinberg Equilibrium Model Archived 2008년 2월 19일 - 웨이백 머신". The synthetic theory of evolution: An introduction to modern evolutionary concepts and theories. Behavioral Sciences Department, Palomar College. Retrieved 2008-01-06.
- ↑ Packer C, Gilbert DA, Pusey AE, O'Brieni SJ. (June 1991). "A molecular genetic analysis of kinship and cooperation in African lions". Nature 351: 562-65. doi:10.1038/351562a0
- ↑ Morjan C, Rieseberg L (2004). "How species evolve collectively: implications of gene flow and selection for the spread of advantageous alleles". Mol. Ecol. 13 (6): 1341–56. doi:10.1111/j.1365-294X.2004.02164.x. PMID 15140081
- ↑ Su H, Qu L, He K, Zhang Z, Wang J, Chen Z, Gu H (2003). "The Great Wall of China: a physical barrier to gene flow?". Heredity 90 (3): 212–9. doi:10.1038/sj.hdy.6800237. PMID 12634804
- ↑ Short RV (1975). "The contribution of the mule to scientific thought". J. Reprod. Fertil. Suppl. (23): 359–64. PMID 1107543
- ↑ 가 나 Gross B, Rieseberg L (2005). "The ecological genetics of homoploid hybrid speciation". J. Hered. 96 (3): 241–52. doi:10.1093/jhered/esi026. PMID 15618301
- ↑ Mavarez, J., Salazar, C.A., Bermingham, E., Salcedo, C., Jiggins, C.D. , Linares, M. (2006) Speciation by hybridization in Heliconius butterflies. Nature.
- ↑ Burke JM, Arnold ML (2001). "Genetics and the fitness of hybrids". Annu. Rev. Genet. 35: 31–52. doi:10.1146/annurev.genet.35.102401.085719. PMID 11700276
- ↑ Wendel J (2000). "Genome evolution in polyploids". Plant Mol. Biol. 42 (1): 225–49. doi:10.1023/A:1006392424384. PMID 10688139.
- ↑ a b Sémon M, Wolfe KH (2007). "Consequences of genome duplication". Curr Opin Genet Dev 17 (6): 505–12. doi:10.1016/j.gde.2007.09.007. PMID 18006297
- ↑ Soltis P, Soltis D (June 2000).The role of genetic and genomic attributes in the success of polyploids Proc. Natl. Acad. Sci. U.S.A. 97 (13): 7051–7. doi:10.1073/pnas.97.13.7051. PMID 10860970
- ↑ Boucher Y, Douady CJ, Papke RT, Walsh DA, Boudreau ME, Nesbo CL, Case RJ, Doolittle WF (2003). "Lateral gene transfer and the origins of prokaryotic groups". Annu Rev Genet 37: 283–328. doi:10.1146/annurev.genet.37.050503.084247. PMID 14616063
- ↑ Walsh T (2006). "Combinatorial genetic evolution of multiresistance". Curr. Opin. Microbiol. 9 (5): 476–82. doi:10.1016/j.mib.2006.08.009. PMID 16942901.
- ↑ Baldo A, McClure M (01 September 1999). Evolution and Horizontal Transfer of dUTPase-Encoding Genes in Viruses and Their Hosts, J. Virol. 73 (9): 7710–21. PMID 104388
- ↑ 가 나 Poole A, Penny D (2007). "Evaluating hypotheses for the origin of eukaryotes". Bioessays 29 (1): 74–84. doi:10.1002/bies.20516. PMID 17187354
- ↑ Whitlock M (01 June 2003). "Fixation probability and time in subdivided populations". Genetics 164 (2): 767–79. PMID 12807795
- ↑ 가 나 Hurst LD (February 2009). "Fundamental concepts in genetics: genetics and the understanding of selection". Nat. Rev. Genet. 10 (2): 83–93. doi:10.1038/nrg2506. PMID 19119264
- ↑ Orr HA (August 2009). "Fitness and its role in evolutionary genetics". Nat. Rev. Genet. 10 (8): 531–9. doi:10.1038/nrg2603. PMID 19546856.
- ↑ Futuyma, Douglas J. (2005). Evolution. Sunderland, Massachusetts: Sinauer Associates, Inc. ISBN 0-87893-187-2.
- ↑ Hoekstra H, Hoekstra J, Berrigan D, Vignieri S, Hoang A, Hill C, Beerli P, Kingsolver J (July 2001). Strength and tempo of directional selection in the wild, Proc. Natl. Acad. Sci. U.S.A. 98 (16): 9157–60. doi:10.1073/pnas.161281098. PMID 11470913
- ↑ Felsenstein (01 November 1979). Excursions along the Interface between Disruptive and Stabilizing Selection, Genetics 93 (3): 773–95. PMID 17248980
- ↑ Andersson M, Simmons L (2006). "Sexual selection and mate choice". Trends Ecol. Evol. (Amst.) 21 (6): 296–302. doi:10.1016/j.tree.2006.03.015. PMID 16769428
- ↑ Kokko H, Brooks R, McNamara J, Houston A (2002). The sexual selection continuum.,Proc. Biol. Sci. 269 (1498): 1331–40. doi:10.1098/rspb.2002.2020. PMID 12079655
- ↑ Hunt J, Brooks R, Jennions M, Smith M, Bentsen C, Bussière L (2004). "High-quality male field crickets invest heavily in sexual display but die young". Nature 432 (7020): 1024–7. doi:10.1038/nature03084. PMID 15616562
- ↑ Lande R (1989). "Fisherian and Wrightian theories of speciation". Genome 31 (1): 221–7. PMID 2687093.
- ↑ Otto S, Whitlock M (01 June 1997). "The probability of fixation in populations of changing size". Genetics 146 (2): 723–33. PMID 9178020
- ↑ Charlesworth B (March 2009). "Fundamental concepts in genetics: Effective population size and patterns of molecular evolution and variation". Nat. Rev. Genet. 10: 195–205. doi:10.1038/nrg2526. PMID 19204717
- ↑ Nei M (2005). "Selectionism and neutralism in molecular evolution". Mol. Biol. Evol. 22 (12): 2318–42. doi:10.1093/molbev/msi242. PMID 16120807
- ↑ Kimura M (1991). "The neutral theory of molecular evolution: a review of recent evidence Archived 2008년 12월 11일 - 웨이백 머신". Jpn. J. Genet. 66 (4): 367–86. doi:10.1266/jjg.66.367. PMID 1954033
- ↑ Kreitman M (August 1996). "The neutral theory is dead. Long live the neutral theory". Bioessays 18 (8): 678–83; discussion 683. doi:10.1002/bies.950180812. PMID 8760341
- ↑ Pulves 외, 이광웅 외 역, 생명 생물의 과학, 2006, 교보문고, ISBN 10-8970855165, 447-448 쪽
- ↑ Scott EC, Matzke NJ (May 2007). "Biological design in science classrooms". Proc. Natl. Acad. Sci. U.S.A. 104 Suppl 1: 8669–76. doi:10.1073/pnas.0701505104. PMID 17494747
- ↑ Hendry AP, Kinnison MT (2001). "An introduction to microevolution: rate, pattern, process". Genetica 112–113: 1–8. doi:10.1023/A:1013368628607. PMID 11838760
- ↑ Leroi AM (2000). "The scale independence of evolution". Evol. Dev. 2 (2): 67–77. doi:10.1046/j.1525-142x.2000.00044.x. PMID 11258392
- ↑ Gould SJ (July 1994). "Tempo and mode in the macroevolutionary reconstruction of Darwinism". Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6764–71. doi:10.1073/pnas.91.15.6764. PMID 8041695. PMC: 44281.
- ↑ Jablonski, D. (2000). "Micro- and macroevolution: scale and hierarchy in evolutionary biology and paleobiology". Paleobiology 26 (sp4): 15–52. doi:10.1666/0094-8373(2000)26[15:MAMSAH]2.0.CO;2
- ↑ Michael J. Dougherty. Is the human race evolving or devolving? Scientific American July 20, 1998.
- ↑ TalkOrigins Archive response to Creationist claims - Claim CB932: Evolution of degenerate forms
- ↑ Carroll SB (2001). "Chance and necessity: the evolution of morphological complexity and diversity". Nature 409 (6823): 1102–9. doi:10.1038/35059227. PMID 11234024
- ↑ Whitman W, Coleman D, Wiebe W (1998). "Prokaryotes: the unseen majority". Proc Natl Acad Sci U S a 95 (12): 6578–83. doi:10.1073/pnas.95.12.6578. PMID 9618454
- ↑ Schloss P, Handelsman J (December 2004). "Status of the microbial census". Microbiol Mol Biol Rev 68 (4): 686–91. doi:10.1128/MMBR.68.4.686-691.2004. PMID 15590780
- ↑ Nealson K (1999). "Post-Viking microbiology: new approaches, new data, new insights". Orig Life Evol Biosph 29 (1): 73–93. doi:10.1023/A:1006515817767. PMID 11536899
- ↑ Buckling A, Craig Maclean R, Brockhurst MA, Colegrave N (February 2009). "The Beagle in a bottle". Nature 457 (7231): 824–9. doi:10.1038/nature07892. PMID 19212400.
- ↑ Elena SF, Lenski RE (June 2003). "Evolution experiments with microorganisms: the dynamics and genetic bases of adaptation". Nat. Rev. Genet. 4 (6): 457–69. doi:10.1038/nrg1088
- ↑ Williams, George C. 1966. Adaptation and natural selection: a critique of some current evolutionary thought. Princeton. "Evolutionary adaptation is a phenomenon of pervasive importance in biology." p5
- ↑ Mayr, Ernst 1982. The growth of biological thought. Harvard. p483: "Adaptation... could no longer be considered a static condition, a product of a creative past, and became instead a continuing dynamic process."
- ↑ Orr H (2005). "The genetic theory of adaptation: a brief history". Nat. Rev. Genet. 6 (2): 119–27. doi:10.1038/nrg1523. PMID 15716908
- ↑ Dobzhansky T. 1968. On some fundamental concepts of evolutionary biology. Evolutionary biology 2, 1–34.
- ↑ Dobzhansky T. 1970. Genetics of the evolutionary process. Columbia, N.Y. p4–6, 79–82, 84–87
- ↑ Dobzhansky T. 1956. Genetics of natural populations XXV. Genetic changes in populations of Drosophila pseudoobscura and Drosphila persimilis in some locations in California. Evolution 10, 82–92.
- ↑ Nakajima A, Sugimoto Y, Yoneyama H, Nakae T (2002). "High-level fluoroquinolone resistance in Pseudomonas aeruginosa due to interplay of the MexAB-OprM efflux pump and the DNA gyrase mutation Archived 2009년 1월 13일 - 웨이백 머신". Microbiol. Immunol. 46 (6): 391–5. PMID 12153116
- ↑ Blount ZD, Borland CZ, Lenski RE (June 2008). "Inaugural Article: Historical contingency and the evolution of a key innovation in an experimental population of Escherichia coli". Proc. Natl. Acad. Sci. U.S.A. 105 (23): 7899–906. doi:10.1073/pnas.0803151105. PMID 18524956
- ↑ Okada H, Negoro S, Kimura H, Nakamura S (1983). "Evolutionary adaptation of plasmid-encoded enzymes for degrading nylon oligomers". Nature 306 (5939): 203–6. doi:10.1038/306203a0. PMID 6646204
- ↑ Ohno S (April 1984). "Birth of a unique enzyme from an alternative reading frame of the preexisted, internally repetitious coding sequence". Proc. Natl. Acad. Sci. U.S.A. 81 (8): 2421–5. doi:10.1073/pnas.81.8.2421. PMID 6585807. PMC: 345072
- ↑ Copley SD (June 2000). "Evolution of a metabolic pathway for degradation of a toxic xenobiotic: the patchwork approach". Trends Biochem. Sci. 25 (6): 261–5. doi:10.1016/S0968-0004(00)01562-0. PMID 10838562
- ↑ Crawford RL, Jung CM, Strap JL (October 2007). "The recent evolution of pentachlorophenol (PCP)-4-monooxygenase (PcpB) and associated pathways for bacterial degradation of PCP". Biodegradation 18 (5): 525–39. doi:10.1007/s10532-006-9090-6. PMID 17123025.
- ↑ Colegrave N, Collins S (May 2008). "Experimental evolution: experimental evolution and evolvability". Heredity 100 (5): 464–70. doi:10.1038/sj.hdy.6801095. PMID 18212804
- ↑ Kirschner M, Gerhart J (July 1998). "Evolvability". Proc. Natl. Acad. Sci. U.S.A. 95 (15): 8420–7. PMID 9671692
- ↑ Gould 2002, pp. 1235–6
- ↑ Piatigorsky J, Kantorow M, Gopal-Srivastava R, Tomarev SI (1994). "Recruitment of enzymes and stress proteins as lens crystallins". EXS 71: 241–50. PMID 8032155
- ↑ Wistow G (August 1993). "Lens crystallins: gene recruitment and evolutionary dynamism". Trends Biochem. Sci. 18 (8): 301–6. doi:10.1016/0968-0004(93)90041-K. PMID 8236445
- ↑ Salesa MJ, Antón M, Peigné S, Morales J (2006). "Evidence of a false thumb in a fossil carnivore clarifies the evolution of pandas Archived 2011년 9월 25일 - 웨이백 머신". Proc. Natl. Acad. Sci. U.S.A. 103 (2): 379–82. doi:10.1073/pnas.0504899102. PMID 16387860
- ↑ 가 나 Fong D, Kane T, Culver D (1995). "Vestigialization and Loss of Nonfunctional Characters". Ann. Rev. Ecol. Syst. 26: 249–68. doi:10.1146/annurev.es.26.110195.001341
- ↑ Jeffery WR (2005). "Adaptive evolution of eye degeneration in the Mexican blind cavefish". J. Hered. 96 (3): 185–96. doi:10.1093/jhered/esi028. PMID 15653557
- ↑ Maxwell EE, Larsson HC (2007). "Osteology and myology of the wing of the Emu (Dromaius novaehollandiae), and its bearing on the evolution of vestigial structures". J. Morphol. 268 (5): 423–41. doi:10.1002/jmor.10527. PMID 17390336
- ↑ Bejder L, Hall BK (2002). "Limbs in whales and limblessness in other vertebrates: mechanisms of evolutionary and developmental transformation and loss". Evol. Dev. 4 (6): 445–58. doi:10.1046/j.1525-142X.2002.02033.x. PMID 12492145
- ↑ Silvestri AR, Singh I (2003). "The unresolved problem of the third molar: would people be better off without it? Archived 2014년 8월 23일 - 웨이백 머신". Journal of the American Dental Association (1939) 134 (4): 450–5. doi:10.1146/annurev.es.26.110195.001341. PMID 12733778
- ↑ Zhang Z, Gerstein M (August 2004). "Large-scale analysis of pseudogenes in the human genome". Curr. Opin. Genet. Dev. 14 (4): 328–35. doi:10.1016/j.gde.2004.06.003. PMID 15261647
- ↑ Hardin G (April 1960). "The competitive exclusion principle". Science 131: 1292–7. PMID 14399717
- ↑ Kocher TD (April 2004). "Adaptive evolution and explosive speciation: the cichlid fish model Archived 2011년 7월 20일 - 웨이백 머신". Nat. Rev. Genet. 5 (4): 288–98. doi:10.1038/nrg1316. PMID 15131652
- ↑ Johnson NA, Porter AH (2001). "Toward a new synthesis: population genetics and evolutionary developmental biology". Genetica 112–113: 45–58. doi:10.1023/A:1013371201773. PMID 11838782
- ↑ Baguñà J, Garcia-Fernàndez J (2003). "o-Devo: the long and winding road. Int. J. Dev. Biol. 47 (7–8): 705–13. PMID 14756346. http://www.ijdb.ehu.es/web/paper.php?doi=14756346.
- Love AC. (2003). "Evolutionary Morphology, Innovation, and the Synthesis of Evolutionary and Developmental Biology Archived 2009년 11월 6일 - 웨이백 머신". Biology and Philosophy 18 (2): 309–345. doi:10.1023/A:1023940220348
- ↑ Allin EF (1975). "Evolution of the mammalian middle ear". J. Morphol. 147 (4): 403–37. doi:10.1002/jmor.1051470404. PMID 1202224
- ↑ Harris MP, Hasso SM, Ferguson MW, Fallon JF (2006). "The development of archosaurian first-generation teeth in a chicken mutant". Curr. Biol. 16 (4): 371–7. doi:10.1016/j.cub.2005.12.047. PMID 16488870
- ↑ Carroll SB (July 2008). "Evo-devo and an expanding evolutionary synthesis: a genetic theory of morphological evolution". Cell 134 (1): 25–36. doi:10.1016/j.cell.2008.06.030. PMID 18614008
- ↑ http://www.nature.com/nature/journal/vaop/ncurrent/full/nature19322.html
- ↑ Wade MJ (2007). "The co-evolutionary genetics of ecological communities". Nat. Rev. Genet. 8 (3): 185–95. doi:10.1038/nrg2031. PMID 17279094
- ↑ Geffeney S, Brodie ED, Ruben PC, Brodie ED (2002). "Mechanisms of adaptation in a predator-prey arms race: TTX-resistant sodium channels". Science 297 (5585): 1336–9. doi:10.1126/science.1074310. PMID 12193784
- ↑ Sachs J (2006). "Cooperation within and among species". J. Evol. Biol. 19 (5): 1415–8; discussion 1426–36. doi:10.1111/j.1420-9101.2006.01152.x. PMID 16910971
- ↑ Paszkowski U (2006). "Mutualism and parasitism: the yin and yang of plant symbioses". Curr. Opin. Plant Biol. 9 (4): 364–70. doi:10.1016/j.pbi.2006.05.008. PMID 16713732
- ↑ Hause B, Fester T (2005). "Molecular and cell biology of arbuscular mycorrhizal symbiosis". Planta 221 (2): 184–96. doi:10.1007/s00425-004-1436-x. PMID 15871030
- ↑ Bertram J (2000). "The molecular biology of cancer". Mol. Aspects Med. 21 (6): 167–223. doi:10.1016/S0098-2997(00)00007-8. PMID 11173079
- ↑ Reeve HK, Hölldobler B (2007). "The emergence of a superorganism through intergroup competition". Proc Natl Acad Sci U S A. 104 (23): 9736–40. doi:10.1073/pnas.0703466104. PMID 17517608.
- ↑ Wilson EO, Hölldobler B (2005). "Eusociality: origin and consequences". Proc. Natl. Acad. Sci. U.S.A. 102 (38): 13367–71. doi:10.1073/pnas.0505858102. PMID 16157878
- ↑ Gavrilets S (2003). "Perspective: models of speciation: what have we learned in 40 years?". Evolution 57 (10): 2197–215. doi:10.1554/02-727. PMID 14628909
- ↑ De Queiroz K (December 2007). "Species concepts and species delimitation". Syst. Biol. 56 (6): 879–86. doi:10.1080/10635150701701083. PMID 18027281
- ↑ de Queiroz K (May 2005). "Ernst Mayr and the modern concept of species". Proc. Natl. Acad. Sci. U.S.A. 102 (Suppl 1): 6600–7. doi:10.1073/pnas.0502030102. PMID 15851674. PMC: 1131873
- ↑ Rice, W.R.; Hostert, E.E. (1993). "Laboratory experiments on speciation: what have we learned in 40 years". Evolution 47 (6): 1637–1653. doi:10.2307/2410209. http://links.jstor.org/sici?sici=0014-3820(199312)47%3A6%3C1637%3ALEOSWH%3E2.0.CO%3B2-T. Retrieved 2008-05-19.
- Jiggins CD, Bridle JR (2004). "Speciation in the apple maggot fly: a blend of vintages?". Trends Ecol. Evol. (Amst.) 19 (3): 111–4. doi:10.1016/j.tree.2003.12.008. PMID 16701238.
- Boxhorn, J (1995). "Observed Instances of Speciation". TalkOrigins Archive. http://www.talkorigins.org/faqs/faq-speciation.html. Retrieved 2008-12-26.
- Weinberg JR, Starczak VR, Jorg, D (1992). "Evidence for Rapid Speciation Following a Founder Event in the Laboratory". Evolution 46 (4): 1214–20. doi:10.2307/2409766
- ↑ 가 나 Herrel, A.; Huyghe, K.; Vanhooydonck, B.; Backeljau, T.; Breugelmans, K.; Grbac, I.; Van Damme, R.; Irschick, D.J. (2008). "Rapid large-scale evolutionary divergence in morphology and performance associated with exploitation of a different dietary resource". Proceedings of the National Academy of Sciences 105 (12): 4792–5. doi:10.1073/pnas.0711998105. PMID 18344323
- ↑ Templeton AR (01 Apr 1980). "The theory of speciation via the founder principle". Genetics 94 (4): 1011–38. PMID 6777243
- ↑ Antonovics J (2006). "Evolution in closely adjacent plant populations X: long-term persistence of prereproductive isolation at a mine boundary". Heredity 97 (1): 33–7. doi:10.1038/sj.hdy.6800835. PMID 16639420
- ↑ Savolainen V, Anstett M-C, Lexer C, Hutton I, Clarkson JJ, Norup MV, Powell MP, Springate D, Salamin N, Baker WJr (2006). "Sympatric speciation in palms on an oceanic island". Nature 441: 210–3. doi:10.1038/nature04566. PMID 16467788
- ↑ Pulves 외, 이광웅 외 역, 생명 생물의 과학, 2006, 교보문고, ISBN 10-8970855165, 427쪽
- ↑ Niles Eldredge and Stephen Jay Gould, 1972. "Punctuated equilibria: an alternative to phyletic gradualism" In T.J.M. Schopf, ed., Models in Paleobiology. San Francisco: Freeman Cooper. pp. 82–115. Reprinted in N. Eldredge Time frames. Princeton: Princeton Univ. Press. 1985
- ↑ Observed Instances of Speciation by Joseph Boxhorn. Retrieved 8 June 2009.
- ↑ Benton MJ (1995). "Diversification and extinction in the history of life". Science 268 (5207): 52–8. doi:10.1126/science.7701342. PMID 7701342
- ↑ Raup DM (1986). "Biological extinction in earth history". Science 231: 1528–33. doi:10.1126/science.11542058. PMID 11542058
- ↑ Avise JC, Hubbell SP, Ayala FJ. (August 2008). "In the light of evolution II: Biodiversity and extinction[깨진 링크(과거 내용 찾기)]". Proc. Natl. Acad. Sci. U.S.A. 105 (Suppl 1): 11453–7. doi:10.1073/pnas.0802504105. PMID 18695213. PMC: 2556414
- ↑ 가 나 Raup DM (1994). "The role of extinction in evolution". Proc. Natl. Acad. Sci. U.S.A. 91 (15): 6758–63. doi:10.1073/pnas.91.15.6758. PMID 8041694
- ↑ Novacek MJ, Cleland EE (2001). "The current biodiversity extinction event: scenarios for mitigation and recovery". Proc. Natl. Acad. Sci. U.S.A. 98 (10): 5466–70. doi:10.1073/pnas.091093698. PMID 11344295
- ↑ Pimm S, Raven P, Peterson A, Sekercioglu CH, Ehrlich PR (2006). "Human impacts on the rates of recent, present, and future bird extinctions". Proc. Natl. Acad. Sci. U.S.A. 103 (29): 10941–6. doi:10.1073/pnas.0604181103. PMID 16829570.
- Barnosky AD, Koch PL, Feranec RS, Wing SL, Shabel AB (2004). "Assessing the causes of late Pleistocene extinctions on the continents". Science 306 (5693): 70–5. doi:10.1126/science.1101476. PMID 15459379
- ↑ Lewis OT (2006). "Climate change, species-area curves and the extinction crisis" (PDF). Philos. Trans. R. Soc. Lond., B, Biol. Sci. 361 (1465): 163–71. doi:10.1098/rstb.2005.1712. PMID 16553315
- ↑ Gould SJ (February 1998). "Gulliver's further travels: the necessity and difficulty of a hierarchical theory of selection". Philos. Trans. R. Soc. Lond., B, Biol. Sci. 353 (1366): 307–14. doi:10.1098/rstb.1998.0211. PMID 9533127
- ↑ Jablonski D (May 2001). "Lessons from the past: evolutionary impacts of mass extinctions". Proc. Natl. Acad. Sci. U.S.A. 98 (10): 5393–8. doi:10.1073/pnas.101092598. PMID 11344284
- ↑ Anja Spang et al. Nature Nature (2015) doi:10.1038/nature14447
- ↑ Isaak, Mark (2005). "Claim CB090: Evolution without abiogenesis". TalkOrigins Archive. http://www.talkorigins.org/indexcc/CB/CB090.html. Retrieved 2008-12-26
- ↑ Peretó J (2005). "Controversies on the origin of life Archived 2015년 8월 24일 - 웨이백 머신" (PDF). Int. Microbiol. 8 (1): 23–31. PMID 15906258
- ↑ Luisi PL, Ferri F, Stano P (2006). "Approaches to semi-synthetic minimal cells: a review". Naturwissenschaften 93 (1): 1–13. doi:10.1007/s00114-005-0056-z. PMID 16292523.
- Trevors JT, Abel DL (2004). "Chance and necessity do not explain the origin of life". Cell Biol. Int. 28 (11): 729–39. doi:10.1016/j.cellbi.2004.06.006. PMID 15563395. Forterre P, Benachenhou-Lahfa N, Confalonieri F, Duguet M, Elie C, Labedan B (1992). "The nature of the last universal ancestor and the root of the tree of life, still open questions". BioSystems 28 (1–3): 15–32. doi:10.1016/0303-2647(92)90004-I. PMID 1337989
- ↑ Joyce GF (2002). "The antiquity of RNA-based evolution". Nature 418 (6894): 214–21. doi:10.1038/418214a. PMID 12110897
- ↑ Trevors JT, Psenner R (2001). "From self-assembly of life to present-day bacteria: a possible role for nanocells". FEMS Microbiol. Rev. 25 (5): 573–82. doi:10.1111/j.1574-6976.2001.tb00592.x. PMID 11742692
- ↑ Penny D, Poole A (1999). "The nature of the last universal common ancestor". Curr. Opin. Genet. Dev. 9 (6): 672–77. doi:10.1016/S0959-437X(99)00020-9. PMID 10607605
- ↑ Bapteste E, Walsh DA (2005). "Does the 'Ring of Life' ring true?". Trends Microbiol. 13 (6): 256–61. doi:10.1016/j.tim.2005.03.012. PMID 15936656
- ↑ Darwin, Charles (1859). On the Origin of Species (1st ed.). London: John Murray. p. 1. Related earlier ideas were acknowledged in Darwin, Charles (1861). On the Origin of Species (3rd ed.). London: John Murray. xiii.
- ↑ Doolittle WF, Bapteste E (February 2007). "Pattern pluralism and the Tree of Life hypothesis". Proc. Natl. Acad. Sci. U.S.A. 104 (7): 2043–9. doi:10.1073/pnas.0610699104. PMID 17261804. PMC: 1892968
- ↑ Kunin V, Goldovsky L, Darzentas N, Ouzounis CA (2005). "The net of life: reconstructing the microbial phylogenetic network". Genome Res. 15 (7): 954–9. doi:10.1101/gr.3666505. PMID 15965028
- ↑ Jablonski D (1999). "The future of the fossil record". Science 284 (5423): 2114–16. doi:10.1126/science.284.5423.2114. PMID 10381868
- ↑ Mason SF (1984). "Origins of biomolecular handedness". Nature 311 (5981): 19–23. doi:10.1038/311019a0. PMID 6472461
- ↑ Wolf YI, Rogozin IB, Grishin NV, Koonin EV (2002). "Genome trees and the tree of life". Trends Genet. 18 (9): 472–79. doi:10.1016/S0168-9525(02)02744-0. PMID 12175808
- ↑ Varki A, Altheide TK (2005). "Comparing the human and chimpanzee genomes: searching for needles in a haystack". Genome Res. 15 (12): 1746–58. doi:10.1101/gr.3737405. PMID 16339373
- ↑ 가 나 Cavalier-Smith T (2006). "Cell evolution and Earth history: stasis and revolution". Philos Trans R Soc Lond B Biol Sci 361 (1470): 969–1006. doi:10.1098/rstb.2006.1842. PMID 16754610
- ↑ Schopf J (1994). "Disparate rates, differing fates: tempo and mode of evolution changed from the Precambrian to the Phanerozoic". Proc Natl Acad Sci U S a 91 (15): 6735–42. doi:10.1073/pnas.91.15.6735. PMID 8041691
- ↑ 《킹.피.셔 과학 백과사전2》. 물구나무. 이름 목록에서
|이름1=이(가) 있지만|성1=이(가) 없음 (도움말) - ↑ Martin W (2005). "The missing link between hydrogenosomes and mitochondria". Trends Microbiol. 13 (10): 457–59. doi:10.1016/j.tim.2005.08.005. PMID 16109488
- ↑ Dyall S, Brown M, Johnson P (2004). "Ancient invasions: from endosymbionts to organelles". Science 304 (5668): 253–57. doi:10.1126/science.1094884. PMID 15073369
- ↑ Lang B, Gray M, Burger G (1999). "Mitochondrial genome evolution and the origin of eukaryotes". Annu Rev Genet 33: 351–97. doi:10.1146/annurev.genet.33.1.351. PMID 10690412.
- McFadden G (1999). "Endosymbiosis and evolution of the plant cell". Curr Opin Plant Biol 2 (6): 513–19. doi:10.1016/S1369-5266(99)00025-4. PMID 10607659
- ↑ DeLong E, Pace N (2001). "Environmental diversity of bacteria and archaea". Syst Biol 50 (4): 470–8. doi:10.1080/106351501750435040. PMID 12116647
- ↑ Kaiser D (2001). "Building a multicellular organism". Annu. Rev. Genet. 35: 103–23. doi:10.1146/annurev.genet.35.102401.090145. PMID 1170027
- ↑ Valentine JW, Jablonski D, Erwin DH (01 Mar 1999). "Fossils, molecules and embryos: new perspectives on the Cambrian explosion". Development 126 (5): 851–9. PMID 9927587
- ↑ Ohno S (1997). "The reason for as well as the consequence of the Cambrian explosion in animal evolution". J. Mol. Evol. 44 Suppl 1: S23–7. doi:10.1007/PL00000055. PMID 9071008.
- Valentine J, Jablonski D (2003). "Morphological and developmental macroevolution: a paleontological perspective". Int. J. Dev. Biol. 47 (7–8): 517–22. PMID 14756327
- ↑ Waters ER (2003). "Molecular adaptation and the origin of land plants". Mol. Phylogenet. Evol. 29 (3): 456–63. doi:10.1016/j.ympev.2003.07.018. PMID 14615186
- ↑ Schloss P, Handelsman J (December 2004). "Status of the microbial census". Microbiol Mol Biol Rev 68 (4): 686–91. doi:10.1128/MMBR.68.4.686-691.2004. PMID 15590780
- ↑
Richard Dawkins, 홍영남 (2006). "이기적 유전자(The Selfish gene)<30주년기념판>". 을유문화사 7-20 ISBN 89-324-7111-8 - ↑ Wright, S (1984). Evolution and the Genetics of Populations, Volume 1: Genetic and Biometric Foundations. The University of Chicago Press. ISBN 0-226-91038-5
- ↑ Zirkle C (1941). "Natural Selection before the "Origin of Species"". Proceedings of the American Philosophical Society 84 (1): 71–123.
- ↑ Muhammad Hamidullah and Afzal Iqbal (1993), The Emergence of Islam: Lectures on the Development of Islamic World-view, Intellectual Tradition and Polity, p. 143-144. Islamic Research Institute, Islamabad.
- ↑ "A Source Book In Chinese Philosophy", Chan, Wing-Tsit, p. 204, 1962
- ↑ Terrall, M (2002). The Man Who Flattened the Earth: Maupertuis and the Sciences in the Enlightenment. The University of Chicago Press. ISBN 978-0-226-79361-0
- ↑ Wallace, A; Darwin, C (1858). "On the Tendency of Species to form Varieties, and on the Perpetuation of Varieties and Species by Natural Means of Selection". Journal of the Proceedings of the Linnean Society of London. Zoology 3: 53–62. doi:10.1098/rsnr.2006.0171. Retrieved 2007-05-13
- ↑ Darwin, Charles (1872). "Effects of the increased Use and Disuse of Parts, as controlled by Natural Selection". The Origin of Species. 6th edition, p. 108. John Murray. Retrieved 2007-12-28
- ↑ Leakey, Richard E.; Darwin, Charles (1979). The illustrated origin of species. London: Faber. ISBN 0-571-14586-8. p. 17-18
- ↑ Ghiselin, Michael T. (September/October 1994), "Nonsense in schoolbooks: 'The Imaginary Lamarck' Archived 2008년 2월 12일 - 웨이백 머신", The Textbook Letter, The Textbook League, retrieved 2008-01-23
- ↑ Magner, LN (2002). A History of the Life Sciences, Third Edition, Revised and Expanded. CRC. ISBN 978-0-8247-0824-5
- ↑ Weiling F (1991). "Historical study: Johann Gregor Mendel 1822–1884". Am. J. Med. Genet. 40 (1): 1–25; discussion 26. doi:10.1002/ajmg.1320400103. PMID 1887835
- ↑ Quammen, D. (2006). The reluctant Mr. Darwin: An intimate portrait of Charles Darwin and the making of his theory of evolution. New York, NY: W.W. Norton & Company
- ↑ Bowler, Peter J. (1989). The Mendelian Revolution: The Emergence of Hereditarian Concepts in Modern Science and Society. Baltimore: Johns Hopkins University Press. ISBN 978-0-8018-3888-0.
- ↑ Pigliucci M (December 2007). "Do we need an extended evolutionary synthesis?". Evolution 61 (12): 2743–9. doi:10.1111/j.1558-5646.2007.00246.x. PMID 17924956.
- Winther RG (August 2008). "Systemic darwinism". Proc. Natl. Acad. Sci. U.S.A. 105 (33): 11833–8. doi:10.1073/pnas.0711445105. PMID 18697926
- ↑ Religious Differences on the Question of Evolution, Pew Forum, 2009-2-4
- ↑ 로널드 L. 넘버스 (2016). 〈1〉. 《창조론자들》. 새물결플러스. ISBN 9791186409558.
- ↑ 진화 이론을 부정하는 주장에 대해서는 다음의 문헌을 참조할 것: Dennett, D (1995). Darwin's Dangerous Idea: Evolution and the Meanings of Life. Simon & Schuster. ISBN 978-0-684-82471-0.
- 이에 대한 19세기 말 ~ 20세기 초의 과학적 반박은 다음의 문헌을 참조할 것: Johnston, Ian C.. "History of Science: Origins of Evolutionary Theory Archived 2017년 1월 7일 - 웨이백 머신". And Still We Evolve. Liberal Studies Department, Malaspina University College. Retrieved 2007-05-24.
- 기타 관련 문헌;
- Bowler, PJ (2003). Evolution: The History of an Idea, Third Edition, Completely Revised and Expanded. University of California Press. ISBN 978-0-520-23693-6.
- Zuckerkandl E (2006). "Intelligent design and biological complexity". Gene 385: 2–18. doi:10.1016/j.gene.2006.03.025. PMID 17011142
- ↑ Scott EC, Matzke NJ (May 2007). "Biological design in science classrooms". Proc. Natl. Acad. Sci. U.S.A. 104 Suppl 1: 8669–76. doi:10.1073/pnas.0701505104. PMID 17494747
- Ross, M.R. (2005). "Who Believes What? Clearing up Confusion over Intelligent Design and Young-Earth Creationism" (PDF). Journal of Geoscience Education 53 (3): 319. Retrieved 2008-04-28.
- Hameed, Salman (2008-12-12). "Science and Religion: Bracing for Islamic Creationism Archived 2014년 11월 10일 - 웨이백 머신". Science 322 (5908): 1637-1638. doi:10.1126/science.1163672. Retrieved 2009.
- ↑ 이른바 인간의 적자생존을 주장한 우생학과 관련해서는 다음 문헌을 참조할 것: Kevles, D (1998). In the Name of Eugenics: Genetics and the Uses of Human Heredity. Harvard University Press. ISBN 978-0-674-44557-4
- ↑ 다윈은 스펜서의 주장과 같이 진화 이론이 사회의 불평등을 정당화하기 위해 악용되는 모든 주장에 대해 강하게 반박하였다. 이와 관련한 문헌은 다음을 참조할 것: Midgley, M (2004). The Myths we Live By. Routledge. p. 62. ISBN 978-0-415-34077-9
- ↑ Allhoff F (2003). "Evolutionary ethics from Darwin to Moore". History and philosophy of the life sciences 25 (1): 51–79. doi:10.1080/03919710312331272945. PMID 15293515.
- Gowaty, Patricia Adair (1997). Feminism and evolutionary biology: boundaries, intersections, and frontiers. London: Chapman & Hall. ISBN 0-412-07361-7.
- ↑ Bull JJ, Wichman HA (2001). "Applied evolution". Annu Rev Ecol Syst 32: 183–217. doi:10.1146/annurev.ecolsys.32.081501.114020
- ↑ Doebley JF, Gaut BS, Smith BD (2006). "The molecular genetics of crop domestication". Cell 127 (7): 1309–21. doi:10.1016/j.cell.2006.12.006. PMID 17190597
- ↑ Jäckel C, Kast P, Hilvert D (2008). "Protein design by directed evolution". Annu Rev Biophys 37: 153–73. doi:10.1146/annurev.biophys.37.032807.125832. PMID 18573077
- ↑ Maher B. (April 2009). "Evolution: Biology's next top model?". Nature 458 (7239): 695–8. doi:10.1038/458695a
- ↑ Borowsky R (January 2008). "Restoring sight in blind cavefish". Curr. Biol. 18 (1): R23–4. doi:10.1016/j.cub.2007.11.023. PMID 18177707
- ↑ Gross JB, Borowsky R, Tabin CJ (January 2009). "A novel role for Mc1r in the parallel evolution of depigmentation in independent populations of the cavefish Astyanax mexicanus". PLoS Genet. 5 (1): e1000326. doi:10.1371/journal.pgen.1000326. PMID 19119422
- ↑ Yergeau DA, Cornell CN, Parker SK, Zhou Y, Detrich HW (July 2005). "bloodthirsty, an RBCC/TRIM gene required for erythropoiesis in zebrafish". Dev. Biol. 283 (1): 97–112. doi:10.1016/j.ydbio.2005.04.006. PMID 15890331
- ↑ Fraser AS (1958). "Monte Carlo analyses of genetic models". Nature 181 (4603): 208–9. doi:10.1038/181208a0. PMID 1350413
- ↑ Rechenberg, Ingo (1973) (in German). Evolutionsstrategie - Optimierung technischer Systeme nach Prinzipien der biologischen Evolution (PhD thesis). Fromman-Holzboog
- ↑ Holland, John H. (1975). Adaptation in Natural and Artificial Systems. University of Michigan Press. ISBN 0-262-58111-6
- ↑ Koza, John R. (1992). Genetic Programming. MIT Press. ISBN 0-262-11170-5
- ↑ Jamshidi M (2003). "Tools for intelligent control: fuzzy controllers, neural networks and genetic algorithms". Philosophical transactions. Series A, Mathematical, physical, and engineering sciences 361 (1809): 1781–808. doi:10.1098/rsta.2003.1225. PMID 12952685
참고 자료[편집]
생물학 일반[편집]
- 조지 B 존슨, 전병학 역, 《생명 과학》, 동화기술, 2007, ISBN 89-425-1186-4
- 말른 호아글랜드, 버트 도드슨, 황현숙 옮김, 《생명의 파노라마》, 사이언스북스, 2001, ISBN 89-8371-050-0
- Pulves 외, 이광웅 외 역, 《생명 생물의 과학》, 2006, 교보문고, ISBN 89-7085-516-5
진화 이론[편집]
- 매트 리들리, 김윤택 역, 《붉은여왕》, 김영사, 2008, ISBN 89-349-2357-1
- 스티븐 제이 굴드, 홍동선 외 역, 《다윈 이후: 생물학 사상의 현대적 해석》, 범양사, 1988, ISBN 89-8371-230-9
- 스티븐 제이 굴드, 김동광 역, 《판다의 엄지》, 세종서적, 1998, ISBN 89-85509-96-9
- 스티븐 제이 굴드, 이명희 역, 《풀하우스》, 사이언스북스, 2002, ISBN 89-8371-089-6
- 리처드 도킨스, 이용철 역, 《이기적인 유전자》, 두산동아, 1997, ISBN 89-00-00347-X
- 스티븐 로즈 외, 이상원 역, 《우리 유전자 안에 없다》, 한울, 1997, ISBN 89-460-2042-3
- 스티븐 존스, 김혜원 역, 《진화하는 진화론》, 김영사, 2008, ISBN 89-349-2869-7
- 최재천 외 18인, 《21세기 다윈 혁명》 , 2014, ISBN 978-89-8371-120-5



![진화상 이기적 유전자의 지배와 인간 개체의 노력을 대비시켜서 무신론을 주장한[191] 리처드 도킨스.](http://upload.wikimedia.org/wikipedia/commons/thumb/3/36/Dawkins_aaconf.jpg/170px-Dawkins_aaconf.jpg)

